Replicación del ADN: procesos monofocales y multifocales
Diapositivas sobre la replicación del ADN. El Pdf detalla la síntesis simultánea, secuencial y bidireccional del ADN, y el mecanismo de alargamiento de los telómeros por la telomerasa. Este material de Biología de nivel universitario incluye diagramas explicativos para facilitar la comprensión del proceso.
Ver más17 páginas

Visualiza gratis el PDF completo
Regístrate para acceder al documento completo y transformarlo con la IA.
Vista previa
Replicación del ADN: Inicio Monofocal o Multifocal
REPLICACIÓN DEL ADN > Inicio monofocal o multifocal · En el cromosoma circular único de los procariotas la replicación comienza siempre en un punto determinado, denominado orige (oric); Se dice que la replicación es monofocal. En consecuencia progresa formando dos horquillas de replicación. · En eucariotas la replicación es multifocal, pues en cada uno de los cromosomas existen múltiples orígenes de replicación (cientos - miles), que dan lugar a un número doble de horquillas
La replicación semiconservadora del DNA es coherente con el modelo de doble hélice hebra nueva 5' 3' hebra nueva hebra hija hebra paterna hebra paterna hebra hijaSíntesis simultánea, secuencial y bidireccional
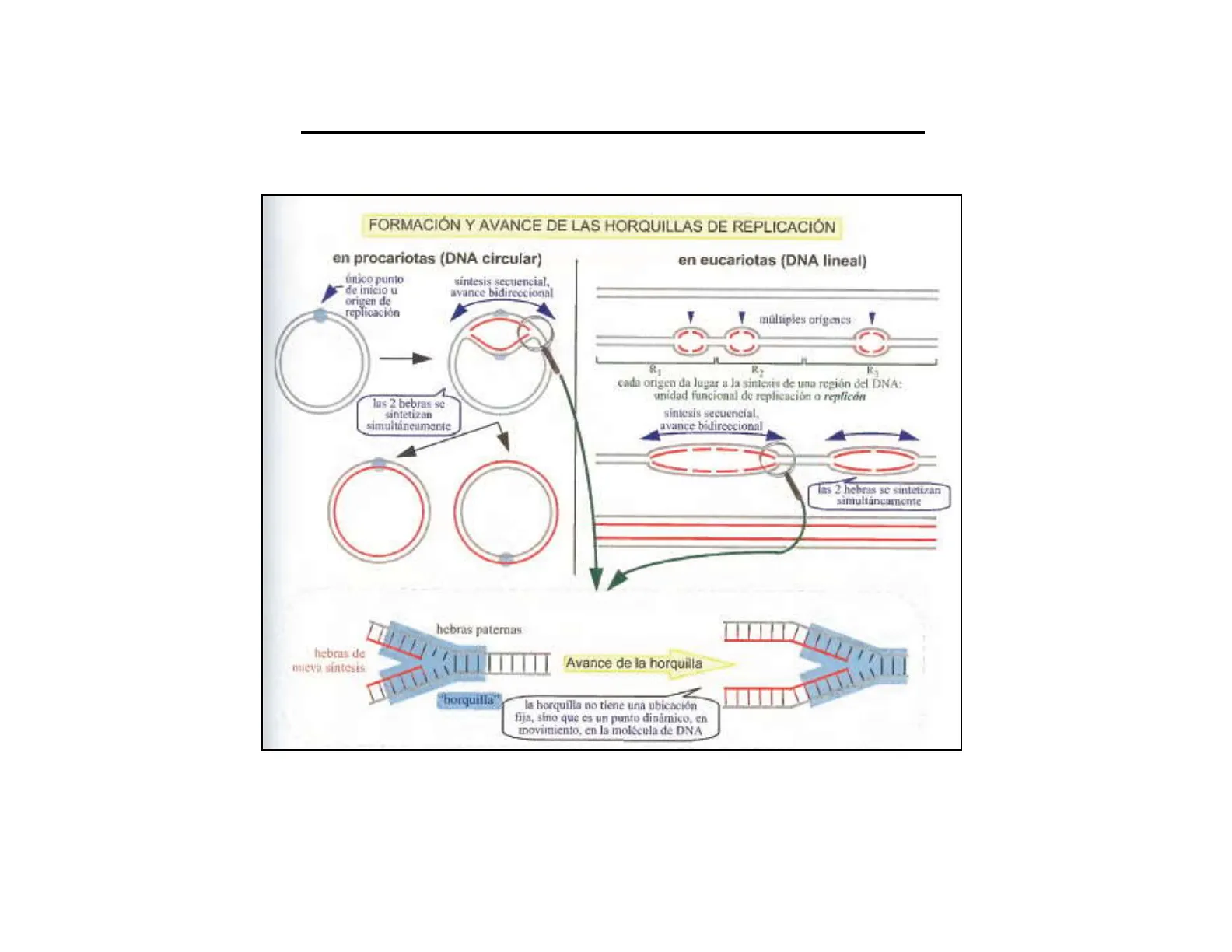
Formación y Avance de las Horquillas de Replicación
FORMACIÓN Y AVANCE DE LAS HORQUILLAS DE REPLICACIÓN en procariotas (DNA circular) en eucariotas (DNA lineal) único punto de inicio u origen de replicación sintesis secuencial, avance bidireccional Y multiples origenes R cada origen da lugar a la sintesis de una región del DNA: unidad funcional de replicación o replicón las 2 bebras se sintetizan simultáneamente sintcsis secuencial avance bidireccional Tas 2 hebras se sintetizan simultaneamente Monofocal Multifocal hebras paternas hebras de mieva sintesis Avance de la horquilla "horquilla" la borquilla no tiene una ubicación fija, sino que es un punto dinámico, en movimiento, en la molécula de DNA
Replicación del ADN en Procariotas
Replicación del ADN en procariotas oriC oriC onC Initiation Elongation oric orIC tr tr tr Elongation ori(* Termination + -onC tr Fig. 16-3 Stages in the replication of a bacterial chromosome. 8 (a)uric ori( Reimtiation unic oriC oriC tr Ir Fig. 16-6 A multiforked chromosome gener- ated by reinitiation of replication at oriC.
Requerimientos de la Reacción de Síntesis de ADN
Requerimientos de la reacción de síntesis de ADN Cebador: Es un fragmento de hebra iniciador, generalmente de ARN, que aporta un grupo 3'- OH libre. La replicación no es autoiniciadora, sino que sólo elonga moléculas preexistente > Sustratos: Cuatros dNTPs: dATP, dGTP, dCTP y dTTp > Cofactores: Mn2+ Mg2+ in vitro. Mg2+ in vivo Molde o plantilla: La incorparción de los DNMPs esta determinada por su complentariedad de bases con la secuencia de cada hebra de ADN que actúa como molde > ADN polimerasa La adición de nucleóticos se realiza siempre sobre el extremo 3'-OH libre. La hebra crece por su extremo 3', y se dice que la síntesis transcurre en dirección 5'-3'.DNA motde, n| dATP + n2 dGTP + n3 dCTP + n4 dTTP DNA + (n)+n2+n3+n4) PP; RNA cebador, Mg2+, DNA polimerasa hebra molde (DNA) 3' 5' 3' 5° G A T A G A T A G C U G C U A A POH -OH -OH -OH 5' 5' (P) (P) P OH OH 5' 3' P dNTP P hebra de DNA en crecimiento (5' ->3')
Mecanismo de la Reacción de Síntesis
MECANISMO DE LA REACCIÓN: nuevo enlace fosfodiéster Base R 3' R3 ataque nuclcofílico del 3'-OH al Pa Base O 0 -dRib HÖ O O- :- dRib 0 O Mg 1 DNA polimerasa O O = ® To-P-O-P-O (PP;) 2 P 11 0 Y Mg2+ pirofosfatasa inorgánica P P P 5' 3' + P P P 13" OH .. P 3 PP. cadena de DNA con N+1 nucleótidos / \3: ÒH 3' OII L -0-0-0-0 -0 cebador (RNA) para la hebra de DNA naciente cadena de N nucleótidos (hebra de DNA naciente) P
Características de la DNA Polimerasa I de E. coli
CARACTERÍSTICAS DE LA DNA POLIMERASA I DE E. coli DNApol-I (unida al DNA) una sola cadena polipeptídica, 103 kDa centro activo 3'-exonucleasa centro activo 5'-exonuclcasa centro active polimerasa (5'->3') Fragmento "grande" o de Klenow N-terminal, 68 kDa. Presenta las actividades polimerasa y 3'-exonuclcasa. Muy bien estudiado, se emplea con frecuencia para la síntesis in vitro de DNA. hebra molde 3' 5' 3' protcolisis con subtilisina o tripsina hebra nueva 5 Fragmento "pequeño" C-terminal, 35 kDa. Sólo muestra la actividad 5'-exonucleasa. Estructura poco conocida. Nucleótido recién incorporado (3'), a punto de unirse a la hebra en crecimiento. Si es erróneo, será eliminado por la actividad 3'-cxonucleasa. El nucleótido 5' terminal, correctamente aparcado, puede ser eliminado por la actividad 5'-exonucleasa.
Características Bioquímicas y Funcionales de las DNA Polimerasas
Algunas características de las DNA polimerasas, desde el punto de vista bioquímico y funcional
Polimerasas en Procariotas y Eucariotas
Polimerasa: I PROCARIOTAS II III a B EUCARIOTAS Y 8 3 Ubicación subcelular núcleo núcleo mito- condria núcleo núcleo Actividades enzimáticas: Primasa (inicio) no no no sí no no no no Polimerasa 5'->3' (elongación) sí si sí si si si si sí 3'-Exonucleasa (o 3'->5') (corrección de pruebas) si sí sí no no si si sí 5'-Exonucleasa (o 5'->3') (eliminación de cebadores) sí no no no no no no no Función en la célula: Replicación (síntesis continuada de hebras nuevas, conductora y retardada) no no sí sólo ini- cialmente no sí sí sí Empalme de fragmentos de Okazaki si sí no no no no si (con nucleasas)
Etapas del Proceso de Replicación
1) Iniciación de la Replicación
1) Iniciación Inicio de la replicación: apertura de la doble hélice en el origen de replicación, creación de dos horquillas de replicación y sintesis de cebadores 3 DNA progenitor, de doble hebra 5 origen de replicación La unión de proteinas de inicio a la secuencia del origen de replicación facilita la separación de las hebras 3 5' 5 Dos moléculas de helicasa inducen la separación de las hebras, inicialmente en el origen y luego avanzando on sentidos opuestos y creando dos horquillas. Las proteínas de unión a hebra sencilla (no mostradas) mantienen las hebras separadas, 3º Dos moléculas de DNApol a/primasn comienzan la sintesis de un RNA cebador para la hebra conductora en cada horquilla3 topoisomerasa RPA, proteina de unión a hebra sencilla 5' helicasa 3' 5' horquilla de replicación dirección de avance Replisoma: Complejo multiproteico que viaja asociado a cada horquilla y realiza la replicación
2) Elongación y Avance de la Horquilla
2) Elongación avance de la horquilla y de la polimerasa hebra conductora: 3 sentido de síntesis y de avance coinciden 5' 5' 3 1 5 11 3' hebra retardada: sentido de síntesis y 32 de avance opuestos 5'
Avance de una de las Horquillas de Replicación
Avance de una de las horquillas de replicación: la síntesis continua de la hebra conductora es simultánea a la sintesis discontinua de la hebra retardada, en fragmentos de Okazaki Para una mejor comprensión se muestran 3 etapas sucesivas en el tiempo (A, B y C) con la síntesis de tres fragmentos (1, 2 y 3) En la hebra conductora se sintetiza un único cebador como punto de partida (extremo 5°) 3 3 5' 5 1 الفا La horquilla de replicación se desplaza continuamente, y a la vez se van sintetizando ambas hebras (por DNApol a. y por DNApol & 01:) La hebra conductora se va elongando de forma continua = cxiremo 3' en crecimiento) B 31 5 2 Una vez terminado el primer fragmento de Okazaki y situado fuera de la horquilla, se está sintetizando el segundo 5' 3º 5' 3 Gracias a que la hebra retardada forma un bucle, la sintesis se puede hacer 5'->3' a la vez que avanza la horquilla 3 5' 3 En esta etapa ya se está sintetizando el tercer fragmento de Okazaki 5 5 5 0 C En la bebra retardada se está sinictizando el primer fragmento de Okazaki = RNA cebador DNA
Organización de Proteínas en la Horquilla de Replicación
Representación global aproximada de la organización de las proteínas responsables de la replicación (componentes del replisoma) en torno a la horquilla de replicación. La situación mostrada corresponde a un momento intermedio de la elongación, con un fragmento de Okazaki sintetizado a medias (p.ej., cl nº 2 en las figuras anteriores, ctapa B). Por claridad, no se muestran otros factores proteicos, como el PCNA que va asociado a las DNApol 8, el sistema de nucleasas FENI/RNasa HI que madura los fragmentos de Okazaki, la DNA ligasa 1, y las topoisomerasas que regulan el superenrollamiento en las dobles hebras progenitora e hijas. La hebra conductora necesita un cebador sólo al comenzar, sintetizado por la actividad primasa de la DNApol & hebra conductora 5' doble hebra hija nº1 La DNApol 8 (o la e) continúa la sintesis de la hebra conductora de forma continua, en sentido 5'->3". recorriendo su hebra molde de 3' a 5" molde de 3' la hebra conductora La DNApol a inicia la elongación, como DNA, del RNA cebador de la hebra conductora helicasa doble hebra progenitora a 8 3ª molde de la hebra 5' conductora 3' RPA, protcina de unión a hebra sencilla 3' molde de la hebra retrasada aqui comenzó el Ju fragmento de Okazaki. y hasta aqui llegará la clongación del 2º (el que 8 esti sintetizando ahora) La hebra retardada necesita un cebador para cada fragmento de Okazaki, sintetizado por la actividad primasa de la DNApol a molde de la hebra retardada (sentido 5'->3' indicado por las flechas azules) 5' 5 hebra retardada (en fragmentos de Okazaki) 3' doble hebra hija nº2 La hebra retardada se sintetiza de forma discontinua, en fragmentos de Okazaki, cada fragmento lo inicia (cebador + DNA) Ja DNApol a y luego lo continua la DNApol 8 (o E), siempre en sentido 5 *- +3". La hebra molde se recorre de 3' a 5' localmente, pero globalmente de 51 a 3'
Maduración de los Fragmentos de Okazaki
Maduración de los fragmentos de Okazaki Maduración de uno de los fragmentos de Okazaki (se representa ya sólo la hebra retardada y su molde) posición de la horquilla 5 3 5 Un sistema de nucicasas (FENI + RNasa HI) elimina el RNA cebador del fragmento nº1 5 3 5 .E 5' La DNApol & o DNApol s elonga el extremo 3' del fragmento nº2, rellenando el lugar que antes ocupaba el cebador, hasta alcanzar el extremo 5' del fragmento nº1 1 3 5'3' 5 La DNA ligasa I sella la mella resultante, uniendo cl 5'-P del fragmento nº1 con el 3'-OH del nº2 5 112)
Replicación de un Cromosoma Eucariota
Representación esquemática de la replicación de un cromosoma eucariota replicón 1 replicón 2 replicón 3 replicón 4 origenes de replicación centromerů telógiera telomero 3 5 3' Retardaita Conductora R C R C 2 avance de les horquillas< Conductora Retardada CR C R aqui se encontrarán las 2 horquillas procedentes de distintos origenes Todos los cebadores intermedios son eliminados por las nucleasas (FENI y RNasa Hi) y sustituidos mediante la elongación del fragmento de Okazaki adyacente. Los cebadores de los extremos 5' de las hebras nuevas, también pueden ser eliminados, pero no. sustituidos; por ello, las hebras'nuevas quedan más cortas en 5' que su molde; .3' 3. 5 El acortamiento de las regiones teloméricas (calculado entre 50-200 pb por cada división celular) es compensado mediante la acción de la enzima telomerasa que alarga los telómero.
Mecanismo de la Telomerasa
Primera Fase (A): La Telomerasa Alarga el Saliente 3'
Primera fase (A): La telomerasa alarga el saliente 3' telómero humano 3 RNA DNA-AATCCCAATCCC (5*) -TTAGGGTTAGGGTTAGGGTTAGGG (3') hTR 5 telomerasa humana repeticiones teloméricas UACAAUCCCAAUCUDAC hTRT proteína saliente 3° (12-16 nt) 3 A1) colocación de la telomerasa 5 DACAAUCCCAAUCUUAC dNTPs aparcamiento de bases entre DNA telomérico y RNA de la telomerasa El componente proteico de la telomerasa cataliza la clongación del saliente 3' empleando como molde la hebra de RNA de la propia telomerasa 5 UA CAAUCCCAAUCUUAC A3) translocación nuevos nucleótidos incorporados- por la telomerasa 3 La telomerasa se desliza sobre el saliente 3' previamente elongado, conservando la complementariedad gracias a la repetición de secuencias 5 DA CAAUCCCAAUGUUAC A4) segunda elongación A-dNTPs De nuevo, la telomerasa elonga el saliente 3', por el mismo mecanismo de la etapa A2 3 UA CAAUCECAAUCHUAC -AATCCCAATCCC -TTAGGGTTAGGGTTAGGGTTAGGGTTAĞGGTTAĞ nuevos nucleótidos incorporados por la telomerasa A5,6 ... ) sucesivas translocaciones y elongaciones -AATCCCAATCCC -TTAGGGTTAGGGTTAGGGTTAGGGTTAGGGTTAGGGTTAGGGTTAGGGTTAGGGTTAG A2) primera elongación -AATCCCAATCCC -TTAGGGTTAGGGTTAGGGTTAGGG 3' -AATCCCAATCCC -TTAGGGTTAGGGTTAGGGTTAGGGTTAG -AATCCCAATCCC -TTAGGGTTAGGGTTAGGGTTAGGGTTAG