Plásmidos o Vectores: elementos extracromosomales autónomos de la UAQ
Diapositivas de la Universidad Autónoma de Querétaro sobre Plásmidos o Vectores. El Pdf detalla los mecanismos de segregación y replicación, con ejemplos de plásmidos lineales y comerciales. Este material de Biología de nivel universitario es útil para comprender conceptos clave.
Ver más52 páginas

Visualiza gratis el PDF completo
Regístrate para acceder al documento completo y transformarlo con la IA.
Vista previa
Universidad Autónoma de Querétaro
UNIVERSIDAD AUTONOMA DE QUERETARO EDUCO EN dONOH 13 NS LA VERDAD 1 Universidad Autónoma de Querétaro Maestría CIEA AS FACULTAD DE NAT TURALES . UAQ
Plásmidos: Elementos Extracromosomales Autónomos
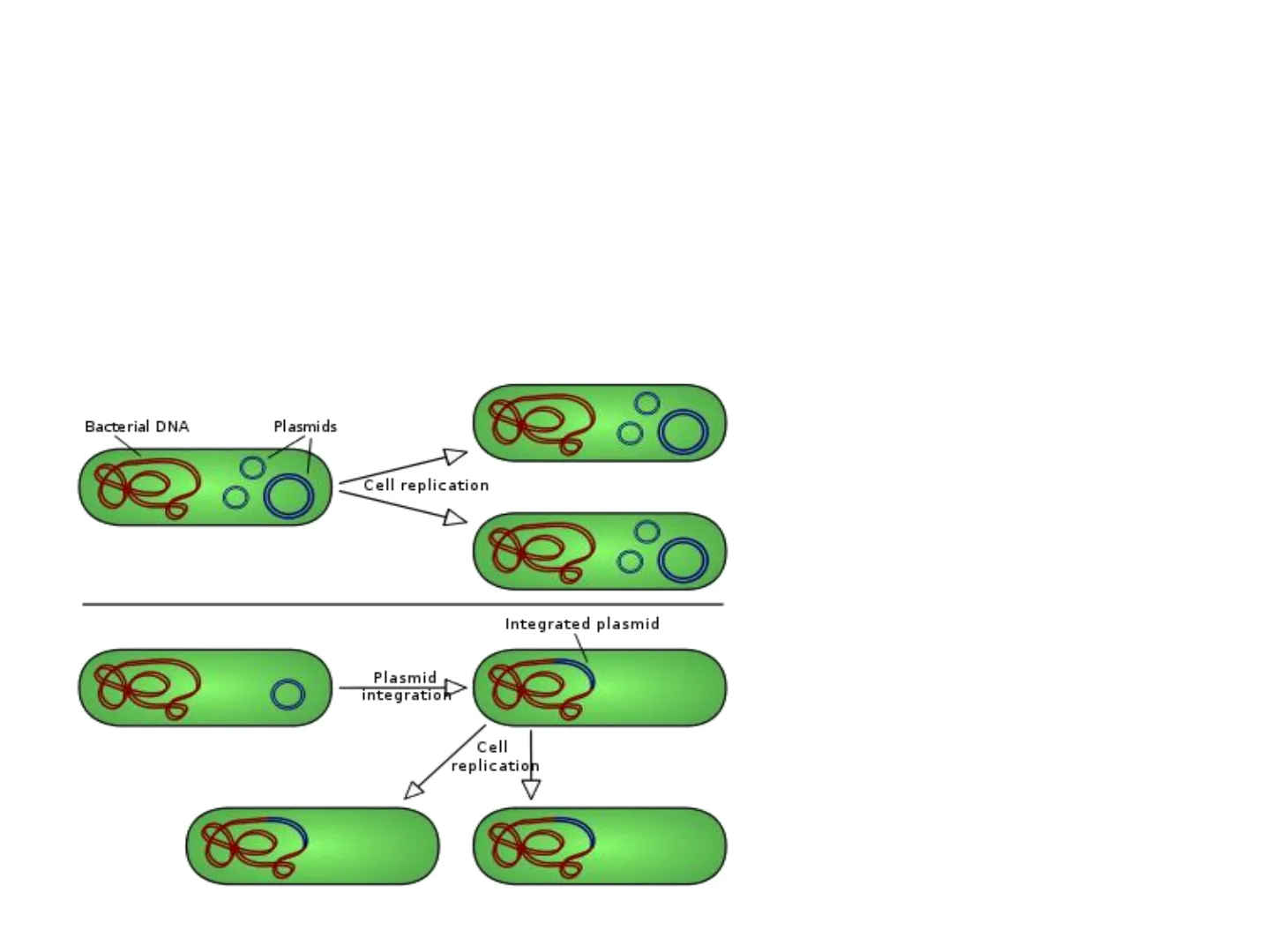
ADN bacteriano Plásmidos Dr. José Antonio Cervantes Chávez. Marzo 6, 2019Definición Moléculas "circulares" de DNA de doble cadena
- extracromosomales y de replicación autónoma. Generalmente presente en procariotes y en algunas levaduras.
Bacterial DNA Plasmids Cell replication Integrated plasmid Plasmid integration Cell replication
Excepciones de Plásmidos
- Excepciones
- Plásmidos Lineales. - Streptomyces spp - Mycobacterium sppCaracterísticas Generales
Características Generales de Plásmidos
- Heredados establemente.
- Tamaño variable, desde 1 Kpb, 1000 Kpb, hasta 14,000 Pkb.
- Transferidos entre un amplio espectro de bacterias - "Promiscuidad". Episomales Integrativos
Bacterial DNA Plasmids Cell replicationRhizobium sp OM ttm
Clasificación de Plásmidos por Función
- "Clasificación con base a su Función"
- Conjugativos . No conjugativoS
- Factor R
- Bacteriocinogenos
- Virulencia
- Tİ
- Simbióticos
- Alto y bajo número de copia.
- Integrativos
- EpisomalesEn ingeniería Genética
Plásmidos en Ingeniería Genética
Fábricas de DNA
Son fábricas de DNA
- Se replican en la bacteria.
- Replicarán el DNA " externo que portan" independientemente del origen.
- Producir grandes cantidades de DNA - casi gratis en función del número de copia - Bajo número 1 por célula - Alto número 50 a 200 por células
La bacteria se reproduce, dando lugar a un gran nuero de bacterias con lanueva característica Estas bacterias produciran la proteína de interés"Transferencia de Plásmido entre Células"
Transferencia de Plásmidos entre Células
0 Recombinant Plasmid E. coli Host Cell Transformed Cell
- Proceso que ocurre de manera natural - Transferencia horizontal - Transferencia vertical
- De manera artificial en el laboratorio. - Choque térmico - Descarga eléctrica. - Ondas de choque
Transfer of a mobile Staphylococcus saprophyticus plasmid isolated from fermented seafood that confers tetracycline resistance. S Lee JH, Heo S, Jeong M, Jeong DW. PLOS One. 2019 Feb 28;14(2):e0213289. doi: 10.1371/journal.pone.0213289. eCollection 2019. PMID: 30818356 Free Article Similar articlesIntercambio de Características Genéticas "Transferencia Horizontal"
Intercambio de Características Genéticas: Transferencia Horizontal
- Transferencia horizontal - Transferencia de material genético de un organismo a otro sin ser de la misma especie.
- Ventajas adaptativas - Sobrevivir a condiciones adversas.
- Fuente de variación genética. - Integración estable-se hereda. - Sustrato para reparar daño a ADN.Aplicaciones en Ingeniería Genética "Vectores"
Aplicaciones de Vectores en Ingeniería Genética
Promotor para estimular expresión génica Gen blanco Plásmido Gen de resistencia a antibióticos
- Indispensables en ingeniería genética. - La detonaron en los años 70's.
- Vehículos para - Clonar genes. - Estudiar la función del gen. - Producción de proteínas recombinantes.
- Terapia génica - Sleepy Beauty - CrisperCasComponentes Estructurales de un plásmido
Componentes Estructurales de un Plásmido
Condiciones Naturales de Plásmidos
Condiciones Naturales
- 1) Origen de Replicación. - Único.
- 2) Marcador Metabólicos - Ventaja bajo presión de selección "natural".
- 3) Sitios de restricción - Distribuídos al azar.
- 4) Transposones - Elementos móviles que migran de su posición original en el genoma o otra.
Aat I Xba | AmpR Hpa | E. coli Ori Pvu II Cla | Sal I Sma | Bam HI1) Origen de Replicación " OriC"
Origen de Replicación "OriC"
1) Origen de Replicación " OriC" Replicación en procariotas: E. coli Tandem array of three 13 bp sequences Binding sites for DnaA protein, four 9 bp sequences - € Consensus sequence GATCTNTTNTTTT Consensus sequence TTATCCACA Oric Origen de replicación ColE1 Origen de replicación DNA de doble hélice 5' 3' 3' 5' Helicasa desenrollando la doble hélice Doble hélice abierta con la ayuda de proteínas iniciadoras ¿Qué otros? 5' 3' 3' 5' Horquilla de replicación Molde de DNA de cadena simple listo para la síntesis de DNA2) Marcador Metabólico
Marcador Metabólico: Resistencia a Antibióticos
2) Marcador Metabólico Factor "R", Resistencia a Antibióticos
- El gen AmpR confiere resistencia a la ampicilina.
- La bacteria que lo posee puede crecer en presencia de este antibiótico.
- La adquisición de este plasmido transforma a una bacteria sensible en resistente. ¿Cómo funciona el gen que confiere resistencia a tetraciclina? ¿ Y el de kanamicina?
amp R gene R. -0 H H HN .CH3 N CH3 0 H OH ₿ lactámico 0 R. 0 R H HN S CH3 B-Lactamase HN CH3 HN CH3 OH H H OH OH 0 HN. S CH3CHCI2 CHCI2 NH NH OH Acetyl- transferases OH OH H3C NO2 NO2 Chloramphenicol NH2 AAC(6') ANT(4') O HO O Aminoglycoside nucleotidyltransferases (ANTs) AMP HO- H2N O AAC(3) H2N NH2 HO ECH3 HO Aminoglycoside phosphotransferases (APHs) 0= HN NH2 ANT(2") OH HO AMP O -OH APH(3') NH-CCH3 Kanamycin B OH Aminoglycoside acetyltransferases (AACs) AAC(2') -OH AAC(3") OH Figure 4. Modification of kanamycin B by aminoglycoside nucleotidyltransferases (ANTs), phosphotransferases (APHs), and acetyltransferases (AACs) [87-91]. HN- OH NH2 CCH3 NH-CCH3 O3) Sitios de reconocimiento para Endonucleasas
Sitios de Reconocimiento para Endonucleasas
3) Sitios de reconocimiento para Endonucleasas Enzimas que cortan dc DNA en secuencias específicas. ¿Función natural? Proteger a la bacterias de ataque virales Eco RI - E = Genero Escherichia - Co = Especie coli - R = Cepa RY13 - I = Orden de descubrimiento Protección vía Metilación Metilasas Viral DNA EcoRV nuclease EcoRV methylase CH3 CH3 CH3 CH3 Bacterial genome DNA duplex KF T G KF 030 050 G restriction enzyme T T A 0JO UJO "sticky ends" 020 C T T À A 050 C¿Cómo se preserva un plásmido en la célula?
Preservación de Plásmidos en la Célula
Mecanismo Tóxina vs Antitoxina
"Mecanismo Tóxina vs Antitoxina
- Estrategia para conservar el plásmido.
- Killer .- mRNA-Toxina
- Antídoto .- RNA antisentido Mejorar imagen
Plasmid makes both kiler and antidoto Kiler Loss of plasmi leaves kiler and antidoto Killerii Antido Antidote decays Killer Killer destroys cell GIIOF 12 14 P¿Cómo se hereda un plásmido?
Herencia de Plásmidos
Sistema de Segregación
- Sistema de Segregación (d) A B 1 A B A) B) S par parA parB Encode proteins that bind to parS parS - cis-acting site on DNA (c) 00 1 PI molecules are located in the center of a dividing cell 00 Partition cell division 0 O MukB recondenses nucleoids after replication Parental nucleoid Condensed daughter Condensed daughter Replication -MukB FIGURE 17.13 The DNA of a single parental nucleoid becomes decondensed during replication. MukB is an essen- tial component of the apparatus that recondenses the daughter nucleoids.Plásmidos de Alto Número de Copia
Plásmidos de Alto Número de Copia
(a) O O C O 20 plasmid molecules 00 40 plasmid molecules 1 O 00 12 plasmid molecules 1 Over replicate O C 28 plasmid molecules Under replicate (bPlásmidos Comerciales
Plásmidos Comerciales
- pMB1
- ColE1
0 2500 HindIII EcoRI EcoRV 1 BamHI 4359 0 29 485 4000 375 Sall PstI 651 tet amp 1000 ori 1000 1500 pBR322_origin T7_promoter M13_forward20_primer M13_pUC_fwd_primer lacZ_a 3925 3602 328 3274 656 PCR2.1 3929 bp 983 Bpil 58 Bvel 219 Pdml 2590 Pstl 5 Alol 284 Bogl 2511 2620 1310 Csp61, Rsal 2474 Tatl, Scal 2473 /16 2782 2292 163 1965 8 HindiIl 624 Pvul 2362 eco47IR Nsbl 2215 NmeAlll 2118 753 Bgll 2109 Cfr101 2075 PlacuVs Mssl 761 Gsul 2080- 1922 Eco311 2062 Bmrl 2040 1762 1148 Munl 892 Eam11051 1990 .Faul 951 BsaXl 955 rep (pMB1) \Drdl 1204 Lgul 979 BoaAl 1588/ Cail 1513 PspFl 1406 Nae | 131 f1 (-) origin Ssp | 442 Ssp | 19 Ssp | 2850 Xmn | 2645 Nae | 330 Sca | 2526 Pvu 1 500 Pvu II 529 Pvu | 2416 Ampr BssH II 619 Kpn | 657 17 pBluescript II SK (+/-) phagemid vector 2961 bp Sac | 759 BssH II 792 T3 Pvu Il 977 ColE1 origin Stratagene Aff III 1153 3000 ori 2000 2395 1 NdeI Faql 103 Adel 120 147 NEOKAN_promoter Bglll (1281) Bell (1286) 328/ bla (ApR) pJET1.2 2974 bp BovCI, Bpu101 717 Mva12691 722 Esp31 739 Mscl (1527) ORF frame 3 NeoR/KanR Nool (1877) lacZ MCS f1 (+) origin IPM MCS 2000 lacZa 396-454 Polylinker 500 amp pUC19 2686 bp pBR322 4361 bp f1_origin
Plásmidos Modificados in vitro
- Los primeros plásmidos modificados in vitro. This Week's Citation Classic ® N Bolivar F, Rodriguez R L. Greene P J, Betlach M C. Heyneker H L, Boyer H W, Crosa J H & Falkow S. Construction and characterization of new cloning vehicles. II. A multipurpose cloning system. Gene 2:95-13, 1977. [Department of Biochemistry and Biophysics, University of California. San Francisco, CA] Made by Mexicans HindIII EcoRI EcoRV 1 1 BamHI 4359 0 29 185 4000 375 SalI PstI 651 3607 tet amp 1000 pBR322 4361 bp 3000 ori 2000 2295 NdeI
- pBR322 - Construído por Bolivar y Rodriguez.
- BamHI esta presente en el gen de resistencia a Tetracilina. La inserción en este sitio inactiva a este gen.
- El plasmido recombinante permitirá que la bacteria crezca solamente en Ampicilina.Serie pUC "University of California"
Serie pUC "University of California"
Apol EcoRI Banll Eco53kl Sacl Acc651 Kpnl Aval Smal Xmal lacZ BamHI MCS Xbal LacR binding site Accl Hincll Sall Plac Amp pUC19 2686 bps BspMI Sbfl Pstl Sphl HindiIl pMB1 ori¿Qué es un Sitio Multiple de Clonación?
Sitio Múltiple de Clonación
- Secuencia corta de nucleótidos para sitios únicos de enzimas de restricción.
- Ubicada en una región específica del plásmido que no interfiere con ninguna función básica del plásmido.
- Ubicados dentro de un marcador de selección "visual".
Xmnl 1994 Scal 1875 Nael 2692 f1 ori 1 start 14 20 Ampr PGEMª-T Vector (3000bp) lacz Ncol 37 Saclı 46 Spel Notl BstZI 55 62 Pall 73 Sall 75 82 94 ori 103 Nsil 112 T SP6 2 3 4 5 6 7 8 9 pUC18 fMET THR MET ILE THR ASN SER (ser ser val pro gly asp pro leu glu es thr cys arg his ala ser leu ala) LEU ALA ATG ACC ATG ATT ACG AAT TCG AGC TCG GTA CCC GGG GAT CCT CTA GAG TCG ACC TGC AGG CAT GCA AGC TTG GCA CTG GCO EcoRI Sstl Kpnl BamHI Xbal Pstl Sphl HindIII Sall Smal Xma Accl Hincll 1 2 3 4 5 6 7 8 9 DUC19 fMET THR MET ILE THR (pro ser leu his ala cys arg ser thr leu glu ed pro arg val pro ser ser) ASN SER LEU ALA ATG ACC ATG ATT ACG CCA AGC TTG CAT GCC TGC AGG TCG ACT CTA GAG GAT CCC CGG GTA CCG AGC TCG AAT TCA CTG GCO HindiIl Sph Pstl Xbal BamHI Kpnl Sstl EcoRI Sall Accl Sma Xmal (b) Hincll 17 1 Apal Aatil Sphl BstZI 26 31 Ndal Sacl BstXI 126Gen Reportero
Gen Reportero
Glucosa presente, lactosa ausente: CAP Promotor Sitio CAP Operador lacZ lacY lacA ARN polimerasa-X Represor Glucosa presente, lactosa presente: CAP Promotor Sitio CAP Operador lacZ lacY lacA ARN polimerasa Represor AlolactosaLa lactosa es hidrolizada por la ß-galactosidasa para generar glucosa y galactosa HOCH2 HO QOH KOH ß-Galactoside linkage HOCH2 OH HO O V O OH 7 H2O OH HOCH2 QOH КОН HO OH CH2 Alolactosa Glucose OH 0 0 H CH2 OH H H H H OH H H OH OH H OH H H OH Lactose La ß galactosidasa también convierte parte de la lactosa en alolactosa OH Galactose ß-Galactosidase KOH HOCH2 HO 0