Replicación y Reparación del ADN en eucariotas, Tecnológico de Monterrey
Diapositivas del Tecnológico de Monterrey sobre la replicación y reparación del ADN. El Pdf explora las teorías de la replicación del ADN, los procesos de iniciación, elongación y terminación en eucariotas, y compara la replicación en eucariotas y procariotas, útil para estudiantes universitarios de Biología.
Ver más17 páginas
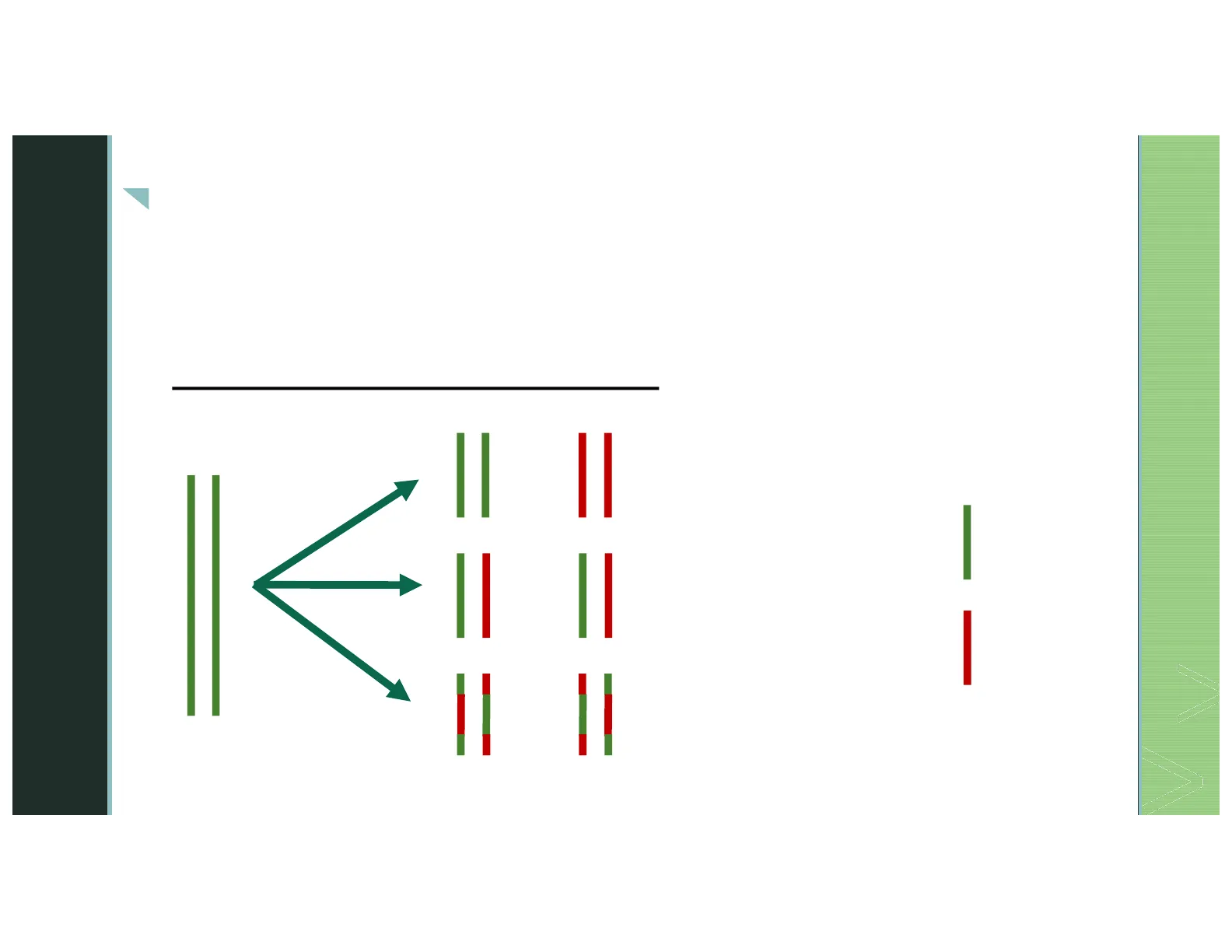
Visualiza gratis el PDF completo
Regístrate para acceder al documento completo y transformarlo con la IA.
Vista previa
Replicación y Reparación del ADN
Teorías de la replicación de ADN
"No se nos ha escapado que el emparejamiento específico (de las bases) que hemos postulado sugiere de inmediato un posible mecanismo de copia del material genético". - Watson y Crick, 1953
Modelos posibles para la replicación del ADN
1. Conservativa V ADN original 2. Semiconservativa ADN nuevo 3. Semiconservativa ADN
El experimento de Meselson-Stahl: Replicación del ADN es semiconservativa
Todo el ADN está inicialmente marcado 15N E.coli 1000 0300 TES N15 Se toma muestra antes de agregar al medio 14N (generación 0) Se agregan células marcadas 15N y se hacen crecer cuatro generaciones N14 = CsCI 0 1 2 3 4 Generación LF ultracentrífuga + Densidad 1 50% 75% 88% N14 100% 50% 25% 12% ..... N15 100% 0 20 40 60 80 Tiempo (min.) Gen 0 Gen 1 Gen 2 Gen 3 Gen 4 . - . - n
Replicación del ADN en procariotas: Iniciación, Elongación y Terminación
Iniciación de la replicación procariota
- Un solo sitio de origen de replicación: oric
- Múltiples sitios de unión para proteína DnaA (iniciadora)
- E. coli posee 11 sitios de unión
- Helicasa DnaC interactúa con DnaA para reclutar a la helicasa DnaB
- Abren cadenas de ADN
Replication of a circular bacterial chromosome + Direction of replication - Figure 15.8a Genomes 4 [ Garland Science 2018) (A) The structure of oriC 20 bp - DNA unwinding element DnaA binding sites
Elongación de la replicación procariota
- Síntesis de dos hebras de ADN
- 5' -> 3'
- Primasa DnaG coloca primer de ARN
- Existen diferentes ADN polimerasa:
- ADN polimerasa I
- Arthur Kornberg y col. (1957) en E. coli
- Actividad exonucleasa (3'-5 y 5'-3' )
- Corrección de errores
- Remoción de primers y adición de bases
(a) 5 Polymerase active site Template Thumb ~3' 5' Primer (b) 5 P3' 5 3'-Exonuclease active site
Elongación con ADN polimerasa III
- ADN polimerasa III: Enzima principal
- 10 diferentes subunidades
- Núcleo polipeptídico:
- a = 5'-3 polimerasa
- £ = 3'-5' exonucleasa
- 0 = Estabiliza ε
- Procesa más de 5 millones de bases
Pol III core flexible linker Y-complex (clamp loader) sliding clamp · DNA ligasa une fragmentos de Okasaki
Terminación de la replicación procariota: Regiones específicas
Terminator sequences in the E.coli genome Origin of replication Terminator sequences Replication forks become trapped in this region Figure 15.18a Genomes 4 (@ Garland Science 2018) Secuencias para terminación The role of Tus Tus proteins 1 The replication fork can pass by a Tus protein bound in one orientation ... 1 ... but is blocked by a Tus protein bound in the other orientation Figure 15.18b Genomes 4 (@ Garland Science 2018) Proteínas "Tus"
Replicación del ADN en eucariotas: Iniciación, Elongación y Terminación
Iniciación de la replicación eucariota
G1 . Muchos ORIs: Humano = 30 mil -50 mil Inicio por acción de ORCs · Complejo helicasa MCM se une · Complejo pre-iniciación G1-S · Topoisomerasa: Evita tensión · ADN polimerasa S · Activación de replicación · 2 horquillas de replicación en cada replicón Ori C Evitan las tensiones debidas a un superenrrollamiento Giras Topoisomeras a Proteínas específicas Proteínas SSB Impiden que el ADN se vuelva a enrollar Helicasa Las proteínas especificas se unen al punto de iniciación La helicasa rompelos enlaces de hidrogeno entre las bases y abre la doble hélice Burbuja de replicación Replication of a linear eukaryotic chromosome + 15.25 kb (yeast) 65-110 kb (humans)
Elongación de la replicación eucariota
- Proceso más complejo que en procariotas
- Diferentes ADN polimerasas
- ADN pol a:
- Inicio de replicación en ORI
- Síntesis de fragmentos de Okasaki
- ADN pol B:
- Reparación por escisión de base
- ADN pol δ ο ε:
- Síntesis cadena líder
- ADN pol Y:
- Enzima de replicación mitocondrial
Priming of DNA synthesis in eukaryotes DNA template 3' 5' - RNA primer New DNA Primase, DNA polymerase a 5' 3' 5' 1 5' 3 5' DNA polymerase & or 8 Figure 15.13b Genomes 4 (@ Garland Science 2018)
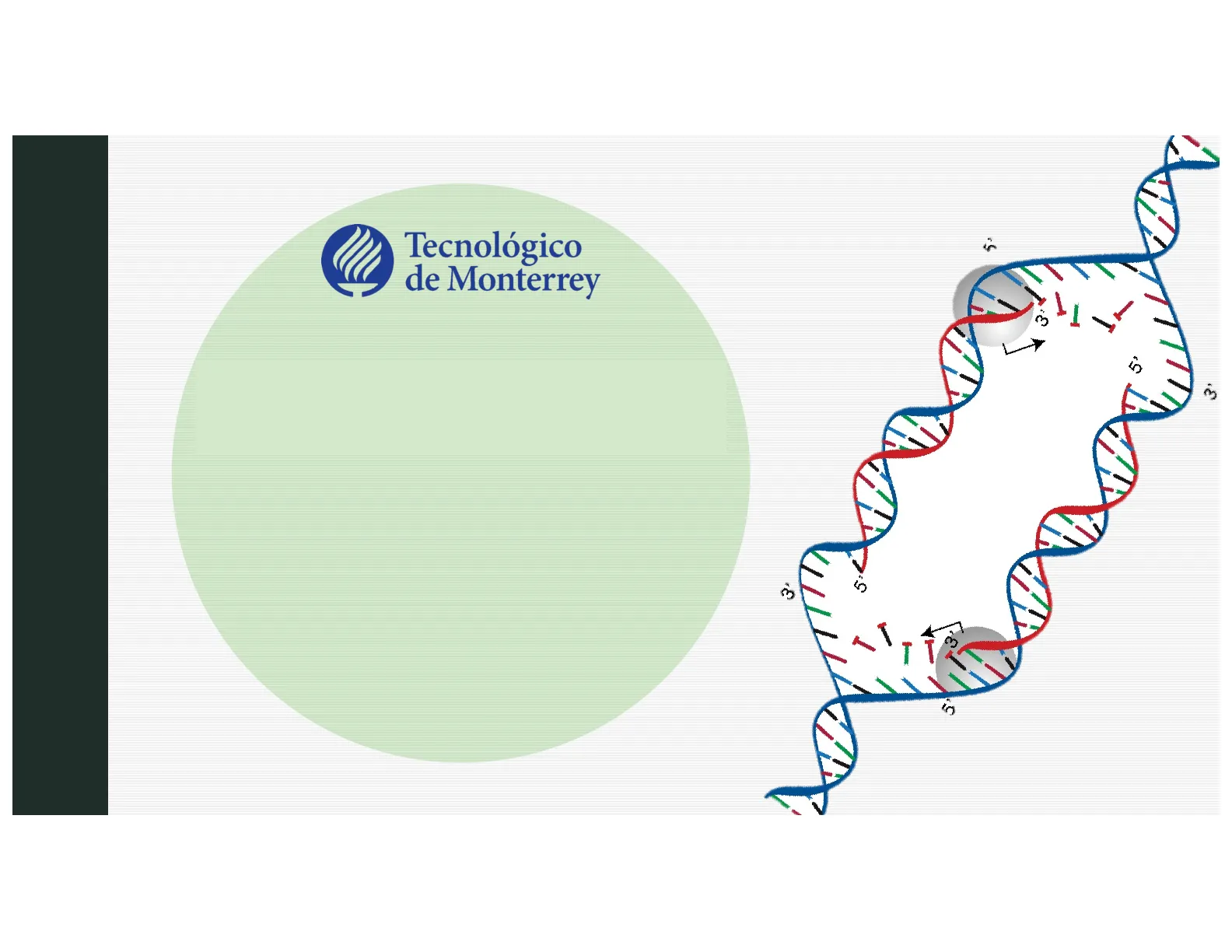
Elongación: Horquilla de replicación
ADN Polimerasa cadena adelantada 5' Topoisomerasa 3' 3' Helicasa 5' cebador Lagging-strand template 5' 5' fragmentos de Okazaki ADN Polimerasa
Terminación de la replicación eucariota
- Sucede en fase S (Interfase)
- Diferentes procesos para terminación:
- Barreras de horquilla de replicación (RFB)
- Terminan o pausan la replicación
- Colisión de horquillas de replicación vecinas
- FEN-1 remueve primers (ARN)
Colisión de 2 horquillas TODO 7 Pol Pol Cac4s Pol Separación de cadenas Pol & Pol & Pol & Coc4s Pol & Terminación de cadenas Pol & Liberación de componentes y con ayuda de Topo II forman cromatina reconstituida Cdc45 Polo Mcm2-7 Pol c Topo I
Terminación: Acción de la telomerasa
3' 5' Secuencia Repetitiva del Telomero Secuencia del primer para que la telomerasa comience Human 5'-TTAGG-3' 5'-CUAACCUAAC-3'
Replicación del ADN en eucariotas vs procariotas
Comparación de replicación
Procariota En citoplasma Primer paso en la fisión binaria Un solo origen de replicación (Ori) 1 replicón Iniciación: DnaA y DnaB (helicasas) Síntesis de cadenas por ADN polimersa III Fragmentos de Okasaki largos: 1000-2000 nt Replicación rápida: 2000 pb/s No hay telomerasa
Eucariota En núcleo Proceso complejo ligado al ciclo celular: Interfase (S) Muchos sitios de origen de replicación en cada cromosoma. Replicación simultánea Muchos replicones Iniciación: Complejo proteico Síntesis de cadena líder: ADN polimerasa o Síntesis de cadena rezagada: ADN polimerasa a Fragmentos de Okasaki cortos: 100-200 nt Replicación lenta: ~ 100 pb/s Telomerasa: Telómeros
Mecanismos de reparación del ADN
Reparación de mal apareamiento
Existen diferentes mecanismos para la reparación y vigilancia de daños al ADN: · Reparación de mal apareamiento · En E. coli se basa por patrón de metilación: · Cadena molde = metilada · MutS/MutH detectan cadena metilada e inician reparación de cadena nueva ADN nuevo 5' 3' G = 3 5' molde ICH3 MutS/MutH 1 5' 3' 3' 5' ICH3 reemplazo de ADN 5' 3' A = = 3 5' ICH3 brecha sellada 1 ICH3 5' 3' A = = T 3' 5' ICH3 La nueva cadena de ADN se corta, y se elimina el nucleótido mal emparejado junto con vecinos ADN polimerasa reemplaza el segmento faltante por los nucleótidos correctos Una ADN ligasa sella la brecha en el esqueleto de ADN Se detecta emparejamiento erróneo en ADN recién sintetizado T T T
Reparación por escisión
· Reparación por escisión: 1. De base 5' 3' U = G 3 5 nucleótidos sin base 5 3 3' 5' 5' 3' 3' 5' El nucleótido sin base se elimina, dejando agujero pequeño en esqueleto de ADN nuevo nucleótido correcto 5' 3' C G 3' 5' ADN polimerasa llena el agujero con la base correcta y la ligasa cierra la brecha 2. De nucleótidos 5' 3' TV A A 3 5' T T 5 3' 3 5' Cuando se detecta el dímero, ADN que lo rodea se abre para formar burbuja T T 5' 3' 11 3' 5' Enzimas cortan la región dañada de la burbuja nuevo ADN sin daño 5' 3' TT A A 3 5' Radiación UV produce un dímero de timina A A G Desaminación convierte base de citosina en uracilo Se detecta y elimina uracilo dejando nucleótido sin base G = A A Un ADN polimerasa reemplaza el ADN escindido (cortado), y una ligasa sella el esqueleto
Reparación de ruptura de la doble cadena
· Reparación de ruptura de la doble cadena: go Ruptura de doble hebra 1. Unión de extremos no homólogos NHEJ 2. Recombinación homóloga Deleciones Molde donante El cromosoma roto se empareja con su homólogo El cromosoma vuelve a pegarse, usualmente con una pequeña mutación en sitio de lisis Inserciones HDR - Inserción o modificación precisa Región dañada se reemplaza por recombinación, usando secuencias copiadas
Bibliografía
- Brown 'Genomes 4', Garland Science
- Garret / Grisham 'Biochemistry' (4th edition) Brooks/Cole, Cengage Learning
- Kunnev et al.(2015). Isolation and sequencing of active origins of DNA replication by nascent strand capture and release (NSCR). J Biol Methods. 2(4): e33.
- Gambus, A. (2017). Termination of Eukaryotic Replication Forks. DNA Replication, 163-187. doi:10.1007/978-981-10-6955-0_8
- Dexheimer, T. S. (2013). DNA repair pathways and mechanisms (Vías y mecanismos de reparación del ADN). En L. A. Matthews, S. M. Cabarcas y E. Hurt (Eds.), DNA repair of cancer stem cells (pp. 19- 32). http://www.springer.com/978-94-007-4589-6.
- Dexheimer, T. S. (2013). DNA repair pathways and mechanisms (Vías y mecanismos de reparación del ADN). En L. A. Matthews, S. M. Cabarcas y E. Hurt (Eds.), DNA repair of cancer stem cells (p. 21). http://www.springer.com/978- 94-007-4589-6.