Replicación de virus ssRNA de cadena positiva: genomas y ciclos
Documento de Universidad sobre Replicación de virus ssRNA de cadena positiva. El Pdf explora la replicación de virus ssRNA de cadena positiva, detallando genomas virales y ciclos de replicación, la síntesis de RNA dependiente de RNA polimerasa, con ejemplos en virus eucarióticos como el del mosaico del bromo y poliovirus, para la asignatura de Biología.
Ver más8 páginas
Visualiza gratis el PDF completo
Regístrate para acceder al documento completo y transformarlo con la IA.
Vista previa
Replicación de virus ssRNA de cadena positiva
Introducción a genomas virales y ciclos de replicación
Tema 5. Replicación de virus ssRNA de cadena positiva (+): Introducción: Genomas virales y ciclos de replicación: Siguiendo el esquema clásico de replicación de los virus. Los virus con genoma de ssRNA de cadena positiva necesitan sintetizar una cadena negativa, de RNA complementario, que sirva como molde para la replicación del genoma del virus. En las células infectadas el ssRNA de cadena positiva será el que nos encontremos en mayor frecuencia, es el que se encapsida.
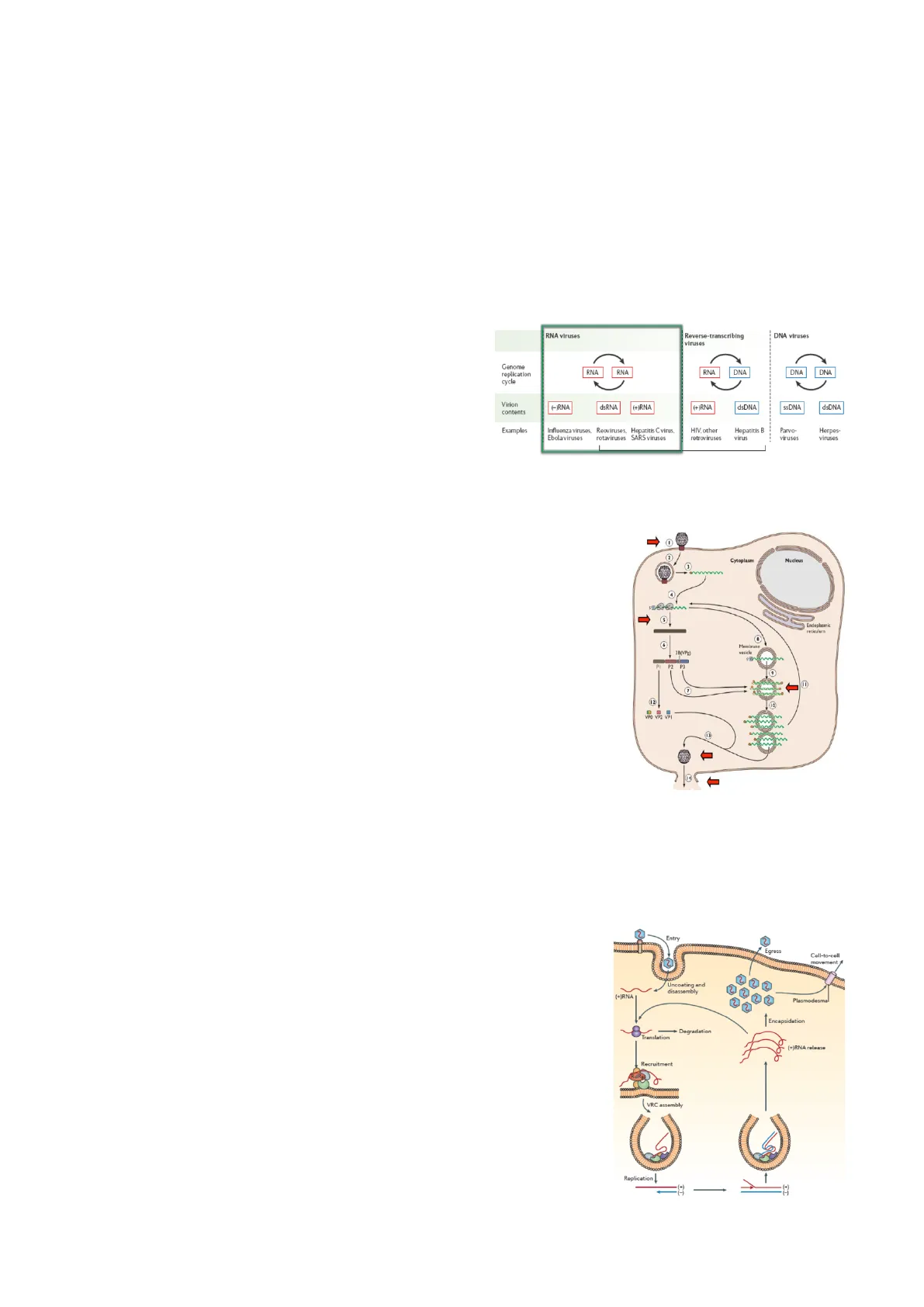
RNA viruses Reverse-transcribing viruses DNA viruses Genome replication cycle RNA RNA DNA DNA Virion contents (-)RNA dsRNA (+)RNA Examples Influenza viruses, Reoviruses, Hepatitis Cvirus, Ebolaviruses rotaviruses SARS viruses HIV. other retroviruses Hepatitis B virus Parvo- viruses Herpes- viruses
Ciclo de infección y replicación de virus de ssRNA (+)
Ciclo de infección y replicación de virus de ssRNA (+): A partir de un ssRNA de sentido mensajero el proceso de infección se simplifica bastante, ya que nada más entrar en la célula puede empezar a traducirse directamente. Lo único que tiene que hacer es producir la copia complementaria de RNA de cadena negativa que le sirva como molde para la síntesis de la cadena positiva. La enzima clave es la RNA polimerasa dependiente de RNA porque el molde es RNA. Esto es importante ya que solo la polimerasa del virus va a ser capaz de iniciar la síntesis de la cadena molde e iniciar la replicación del genoma. En algunas plantas se ha visto que hay RNA polimerasas dependientes de RNA, pero que no tienen capacidad de iniciar, sólo de elongar. La replicación de estos virus ocurre en el citoplasma y siempre tiene que estar asociada a una membrana del huésped (del retículo endoplasmico, lisosoma, peroxisoma, etc.). De esta manera, se van a formar una especie de complejos de replicación que son unas vesículas que protegen el evento de síntesis de las nuevas cadenas del RNA viral. Al entrar el virus en una célula eucariota, tiene que multiplicarse para poder realizar todas sus tareas, de manera que el RNA del virus sigue dos vías: la traducción de las proteínas implicadas en la replicación y, por otro lado, las proteínas implicadas en la replicación van a formar un complejo de replicación asociado a un sistema membranoso de la célula huésped. De esta manera, estos eventos tienen que individualizarse, lo cual se consigue gracias a la asociación con el sistema membranoso porque se produce una compartimentalización que permite separar los RNAs que se están replicando de los que se están traduciendo. En resumen, en un virus ssRNA (+) animal, el mRNA se libera y se sintetizan las proteínas implicadas en la replicación en el citosol. Comienza entonces Entry 2 Egress Cell-to-cell movement Uncoating and disassembly (+)RNA 12 Plasmodesma Encapsidation + Degradation Translation (+)RNA release Recruitment RdR VRC assembly Replication - EI G Endoplasmic reticulum Membrane vesicle JB(VPg) PI P2 P3 1 12 VPO VP2 VPI 2 Cytoplasm Nucleus RNA DNA SSDNA dsDNA (+)RNA dsDNAel reclutamiento de los factores del huésped y la asociación con una membrana, ensamblándose el complejo de replicación que se compartimentaliza y empieza la replicación del virus en el complejo (la replicación nunca ocurre libre en el citosol, siempre tiene que estar protegida por una membrana). Por otro lado, el mRNA mensajero se libera y se puede encapsidar con todas las proteínas que vienen de la traducción del genoma.
Síntesis de RNA dependiente de RNA
Síntesis de RNA dependiente de RNA: Generalmente, cuando se produce la síntesis de un RNA que proviene de un RNA, se tiene que iniciar y terminar en sitios específicos del molde. Como los virus no tienen telómeros ni centrómeros, toda la información del genoma va a ser copiada, no sobra nada. La RNA polimerasa dependiente de RNA (RdRp) puede iniciar la síntesis de novo o puede requerir un cebador (péptido). Además, es muy importante que sea capaz de diferenciar entre el RNA viral y los RNAs de la célula hospedadora (no puede replicar todo lo que encuentre en sentido positivo), y entre cadenas de sentido negativo y de sentido positivo (primero sintetiza la cadena negativa para utilizarla como molde para la replicación). Tiene que producir más RNA de cadena positiva que de cadena negativa (100 veces más) porque es la que se encapsida y, por lo tanto, tiene que ser mayoritaria. Por otro lado, se ha visto que en algunos casos se pueden requerir otras proteínas virales y del huésped, además de la RdRp viral. La cadena del RNA se sintetiza por una incorporación sucesiva de nucleótidos del huésped dirigida por el molde, es decir, se van añadiendo los nucleótidos al extremo 3'OH marcando el sentido de 3' a 5'. Sin embargo, puede ocurrir también una síntesis de RNA no mediada por el molde, pero principalmente sucede en los virus de ssRNA de cadena negativa (emplean un cebador). Esto no tiene por qué darse siempre, ya que puede haber síntesis de RNA no mediada por el molde, común entre los virus de cadena negativa (usan un cebador).
Tipos de iniciación de la síntesis de RNA
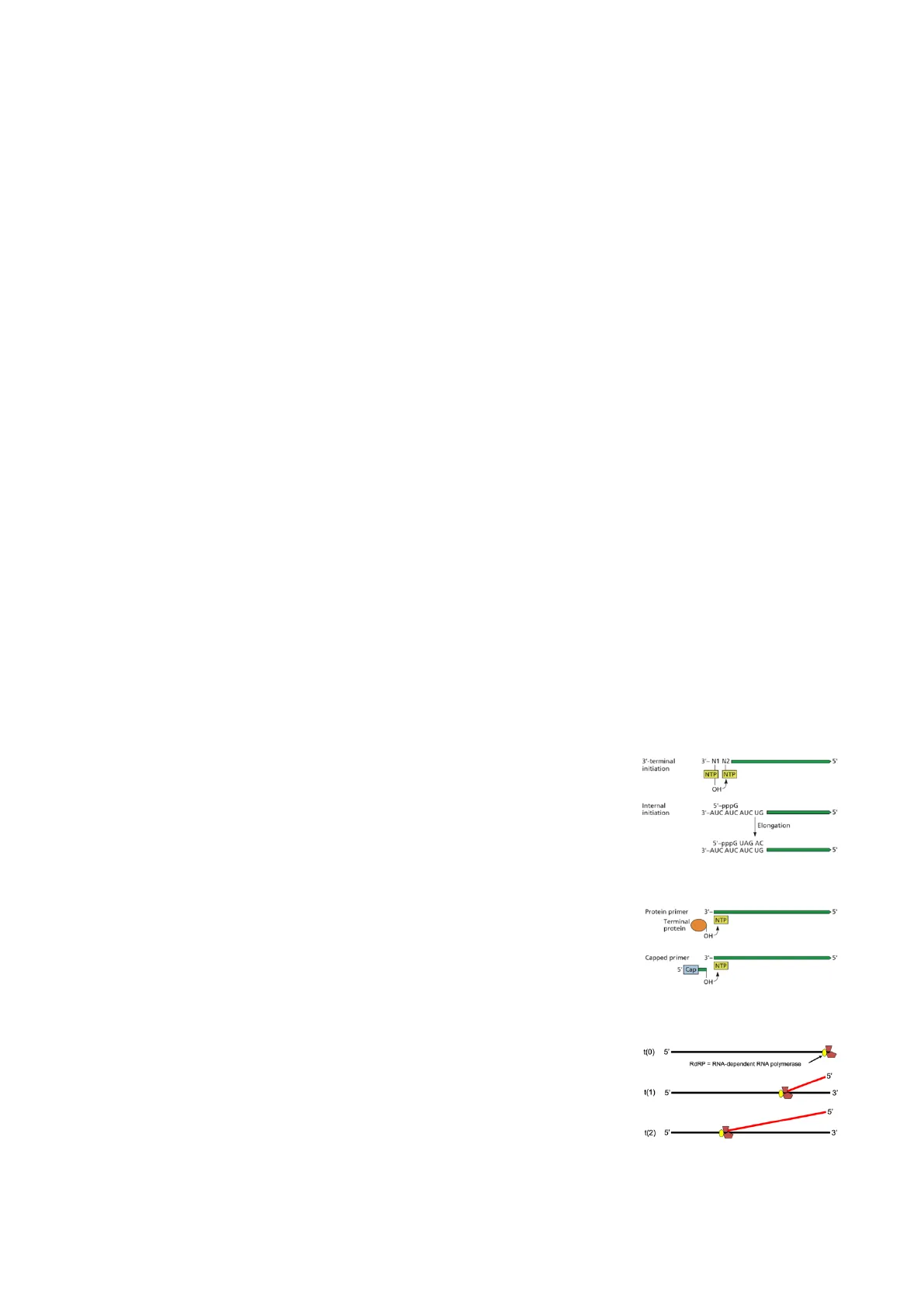
Podemos distinguir dos tipos de iniciación de la síntesis de RNA:
- Iniciación de novo: la síntesis no necesita ningún cebador, sino que simplemente se une la RNA polimerasa y utiliza el molde para incorporar nucleótidos. La síntesis del RNA puede comenzar en el extremo 3', generando la cadena complementaria, o a partir de una iniciación interna para dar lugar a un RNA subgenómico.
- Iniciación dependiente del uso de un cebador: el virus no utiliza un péptido para empezar la síntesis del RNA, sino que siempre utiliza una proteína. Por otro lado, en otros casos que no son virus de ssRNA de cadena positiva, se puede utilizar una estructura derivada de los mRNAs del huésped, un capped primer.
La lectura siempre se tiene que iniciar del extremo 3' al extremo 5', ya que se necesita un extremo 3' OH libre para ir añadiendo los nucleótidos y sintetizar la cadena complementaria. De esta manera, la dirección de crecimiento de la nueva cadena siempre es 5' > 3', es decir, el movimiento del complejo de transcripción por la cadena molde es 3' > 5' y la polaridad de la cadena naciente es 5' -> 3'.
3'-terminal initiation 3'- N1 N2 5 NTP NTP OH Internal initiation 5'-pppG 3'-AUC AUC AUC UG 5 Elongation 5'-pppG UAG AC 3'-AUC AUC AUC UG 5' 3' 5' Protein primer Terminal protein NTP OH 3º- 5 Capped primer NTP Cap OH t(0) 5 RdRP = RNA-dependent RNA polymerase 5" t(1) 5' 3' 5' t(2) 5' 3' 5Además, la replicación es asimétrica, es decir, no ocurre de manera semiconservativa como en los mRNA celulares. Esto es bueno para los virus porque sus polimerasas no tienen sistema de corrección de error de lectura (a excepción de los nidovirales) y este método de replicación favorece que no se acumulen demasiados errores. En este caso, la cadena positiva sirve de molde, con iniciación de novo o dependiente de primer, para la síntesis de la cadena complementaria negativa. Una vez que se empieza la síntesis de la cadena complementaria en el extremo 3' de la cadena positiva, se une otro complejo de replicación y 5' 5'4- 3" 5 5'- + así sucesivamente, es decir, a partir de una sola molécula de RNA molde Synthesis of Minus-Strand Intermediates By RdRp Synthesis of Synthesis of Minus-Strand By RdRp Plus-Strand Progeny RNAS se generan muchas copias de la cadena complementaria (así se evita or cometer errores). De igual manera, la cadena complementaria sirve como - 5' '5' 5 molde para la síntesis del RNA viral y sucede lo mismo, de modo que se 3 3' 5' 3' 5' 3 5º Genomic RNA (+SsRNA) Replicative Form (dsRNA) Replicative Intermediate I utiliza una sola cadena como molde para la síntesis de varias cadenas. Replicative Intermediate II Los errores que cometen las polimerasas son del orden de 10-4 a 10-5, es decir, comete muchos errores por ronda de replicación, pero como la replicación es asimétrica estos errores no se van acumulando porque unos complejos lo cometen en una cadena y otros en otra (el error no se conserva). Durante el proceso se genera una forma replicativa de dsRNA, aunque también se han visto intermediarios en los que hay parte de doble cadena y parte de cadena simple. La célula en condiciones normales nunca tiene dsRNA en cantidades suficientes para ser detectado, de manera que solo cuando hay una infección por virus podemos detectar dsRNA en la célula como intermediario de la replicación del virus.
Replicación del RNA del fago QB
Replicación del RNA del fago QB: Cuando los virus van a empezar su replicación, codifican para su replicasa (RdRp) y otras actividades como la metiltransferasa y helicasa, pero todo esto va acompañado por un conjunto de proteínas del huésped, conformando el complejo de replicación del virus. De este modo, la replicasa no es el único factor implicado en el complejo, lo cual dificulta considerablemente su aislamiento para el estudio de las proteínas implicadas en el complejo de replicación. Gracias al aislamiento de la actividad replicasa del fago Qß (es un complejo que se puede extraer de bacterias infectadas para poder estudiarlo in vitro) se avanzó mucho en el conocimiento de cómo funciona el complejo de replicación en un virus de este tipo, que en este caso infecta a procariotas. En estos estudios se dilucidó que la síntesis se iniciaba de novo en el extremo 3' sin el uso de cebadores y que el complejo de replicación era capaz de distinguir entre el RNA viral y el RNA celular, así como el sentido de la cadena, es decir, que la polimerasa era específica para el material genético del virus. A medida que se estabiliza el complejo de replicación, el proceso de síntesis se da de manera más rápida. Inicialmente, llega la polimerasa, reconoce su molde y, como no hay PppGG- cebador, la unión entre la polimerasa y el molde es bastante inestable pppGG~N7 porque cualquier cambio puede hacer que la polimerasa se separe. Al CTP ATP PppGG GTP Transition 2 ser tan inestable, la síntesis del primer nucleótido es la más lenta y or GTP,UTP conforme se van añadiendo más nucleótidos la unión comienza a ser Template Transition 1 RdRp Stability más estable porque aumenta la longitud del "cebador" y el proceso va siendo más rápido hasta copiar la cadena completa.