Inmunidad innata: respuestas principales, sistema del complemento y pentraxinas
Diapositivas de Ucam Universidad Católica de Murcia sobre Inmunidad Innata. El Pdf, un recurso de Biología para Universidad, detalla las respuestas principales como inflamación y defensa antiviral, incluyendo el sistema del complemento y las pentraxinas.
Ver más41 páginas

Visualiza gratis el PDF completo
Regístrate para acceder al documento completo y transformarlo con la IA.
Vista previa
Inmunidad Innata
TEMA 3 INMUNOLOGÍA 2º FARMACIA SAN A UNIVERSID NTONIO & UCAM UNIVERSIDAD CATÓLICA DE MURCIA ANO MCMXCVI
Principales Respuestas Inmunitarias
- INFLAMACIÓN
- DEFENSA ANTIVÍRICA
- ESTÍMULO DE LA INMUNIDAD ADAPTATIVA
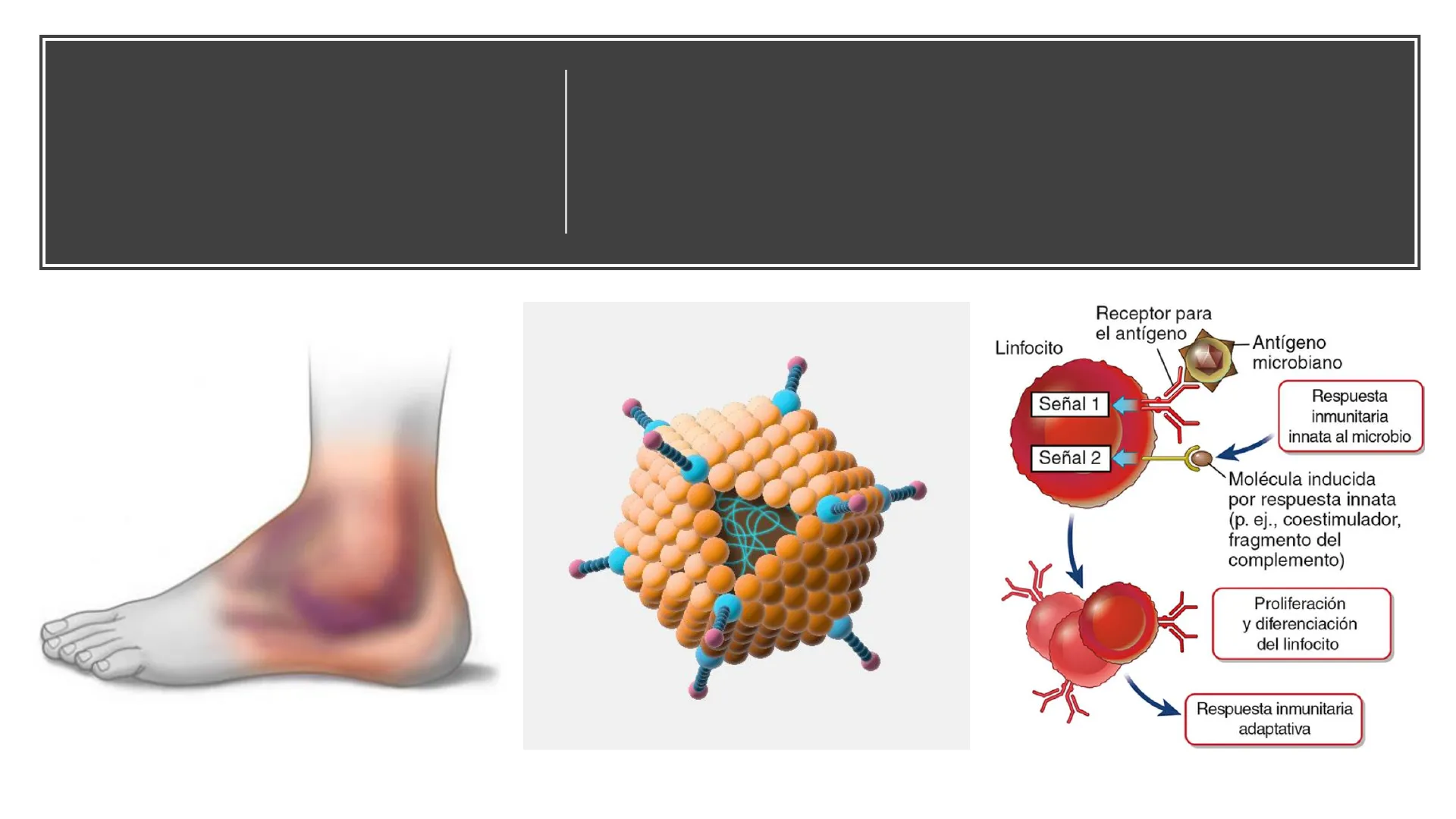
Receptor para el antígeno Linfocito -Antígeno microbiano Señal 1 Respuesta inmunitaria innata al microbio Señal 2 Molécula inducida por respuesta innata (p. ej., coestimulador, fragmento del complemento) Proliferación y diferenciación del linfocito Respuesta inmunitaria adaptativa
Funciones de la Inmunidad Innata
- Las defensas físicas y químicas en las barreras epiteliales, como la piel y el recubrimiento de los sistemas digestivo y respiratorio, bloquean la entrada de microbios.
- Las respuestas inmunitarias innatas son la primera reacción a los microbios, que sirven para controlar o eliminar la infección del hospedador frente a muchos microorganismos patógenos.
- La inmunidad innata elimina las células dañadas e inicia el proceso de reparación tisular.
- Las respuestas inmunitarias innatas estimulan las respuestas inmunitarias adaptativas y pueden influir en la naturaleza de las respuestas adaptativas para hacerlas eficaces de forma óptima frente a diferentes tipos de microbios.
Diferencias entre Inmunidad Innata y Adaptativa
Especificidad de la Inmunidad
Inmunidad innata Frente a estructuras compartidas por clases de microbios (patrones moleculares asociados a microor- ganismos patógenos) DIFERENCIAS INNATA y ADAPTATIVA Diferentes microbios - Receptores tipo lectina idénticos
Inmunidad adaptativa Frente a detalle estructural de moléculas microbianas (antige- nos); pueden reconocer antíge- nos no microbianos Diferentes microbios Moléculas de anticuerpo distintas
Número de Moléculas Reconocidas
Número de moléculas microbianas reconocidas Alrededor de 1.000 patrones mole- culares (estimados)
>107 antígenos
Receptores Inmunitarios
Receptores Codificados en línea germinal; di- versidad limitada (receptores para el reconocimiento de patrones)
Codificados por genes pro- ducidos por recombinación somática de segmentos géni- cos; mayor diversidad lg Receptor tipo Toll Receptor para N-formil metionilo Receptor Receptor para manosa basurero TCR pood good
Tipos y Distribución de Receptores
DIFERENCIAS INNATA y ADAPTATIVA Inmunidad innata Número y tipo de recep- tores <100 tipos diferentes de receptores invariantes Distribución de recep- tores No es clonal: receptores idénticos en todas las células de la misma línea
Inmunidad adaptativa Solo 2 tipos de receptores (Ig y TCR), con millones de va- riantes cada uno Clonal: clones de linfocitos con diferentes especificidades ex- presan diferentes receptores
Genes Codificadores de Receptores
Genes codificadores de receptores Codificados en línea germinal, en todas las células
Formado por recombinación somática de segmentos génicos solo en linfocitos T y B
Discriminación entre lo Propio y lo Ajeno
Discriminación entre lo propio y lo ajeno Sí; las células sanas del hospe- dador no se reconocen o pueden expresar moléculas que impidan las reacciones inmunitarias innatas
Sí; en función de eliminación o inactivación de linfocitos autor- reactivos; puede ser imperfecta (lo que da lugar a autoinmuni- dad)
Patrones Moleculares Asociados a Microorganismos Patógenos (PAMP)
El sistema inmunitario innato reconoce estructuras moleculares que son producidas por los microorganismos patógenos Patrones moleculares asociados a microorganismos patógenos (PAMP, pathogen-associated molecular patterns)
Tipos de PAMP
Patrones moleculares asociados a microorganismos patógenos Ácidos nucleicos ARNmc: virus ARNbc: virus CpG no metilado: virus, bacterias Proteínas Pilina: bacterias Flagelina: bacterias Lípidos de la pared celular LPS: bacterias gramnegativas Ácido lipoteicoico: bacterias gramposi- tivas Glúcidos Manano: hongos, bacterias Glucanos: hongos
Patrones Moleculares Asociados a Lesión (DAMP)
El sistema inmunitario innato reconoce moléculas endógenas que producen o liberan células dañadas o que se están muriendo · Patrones moleculares asociados a lesión (DAMP, damage- associated molecular patterns)
Ejemplos de DAMP
Patrones moleculares asociados a lesión Proteínas inducidas por estrés HSP Cristales Urato monosódico Matriz extracelular sometida a proteolisis Péptidos proteoglucanos Componentes de mitocondrias que se en- cuentran fuera de las mitocondrias Péptidos formilados extracelulares y ATP Proteínas nucleares o ácidos nucleicos que se encuentran fuera del núcleo HMGB1 extracelular, histonas o ADNbc citoplasmático
Receptores de Reconocimiento de Patrón
Receptores Asociados a Células
RECEPTORES DE RECONOCIMIENTO DE PATRÓN Asociados a células
Asociados a células Localización Ejemplos específicos Ligandos para PAMP o DAMP
TLR (Receptores Tipo Toll)
TLR Membrana plasmática y membranas endosómicas de DC, fagocitos, células endoteliales, linfocitos B y otros muchos tipos celulares TLR 1-9 Varias moléculas microbianas, como el LPS bacteriano, los pep- tidoglucanos, los ácidos nucleicos víricos
NLR (Receptores Tipo NOD)
NLR Citosol de fagocitos, células epiteliales y otras células NOD1/2 Peptidoglucanos de pared celular bacteriana Familia NLRP (infla- mosomas) Cristales intracelulares (urato, sílice); cambios en el ATP citosó- lico y las concentraciones iónicas; daño lisosómico
RLR (Receptores Tipo RIG)
RLR Citosol de fagocitos y otras células RIG-1, MDA5 ARN vírico
CDS (Detectores de ADN Citosólico)
CDS Citosol en muchos tipos de células AIM2; CDS asociados a STING ADN vírico y bacteriano
CLR (Receptores Tipo Lectina C)
CLR Membranas plasmáticas de fagocitos Receptor para manosa, DC-SIGN Glúcidos de superficie microbiana con manosa y fucosa terminales Dectina 1, dectina 2 Glucanos presentes en paredes celulares de hongos y bacterias
Receptores Basurero
Receptores basurero Membranas plasmáticas de fagocitos CD36 Diacilglicéridos microbianos
Receptores para N-formil met-leu-fe
Receptores para N-formil met-leu-fe Membranas plasmáticas de fagocitos FPR y FPRL1 Péptidos que contienen N- formilmetionil
Receptores Solubles
RECEPTORES DE RECONOCIMIENTO DE PATRÓN Solubles
Solubles Localización Ejemplos específicos Ligandos para PAMP o DAMP
Pentraxinas
Pentraxinas Plasma Proteína C reactiva Fosforilcolina y fosfatidiletanola- mina microbianas
Colectinas
Colectinas Plasma Lectina ligadora de manosa Glúcidos con manosa y fucosa terminales Alveolos SP-A y SP-D Varias estructuras microbianas
Ficolinas
Ficolinas Plasma Ficolina N-acetilglucosamina y ácido lipo- teicoico de las paredes celulares de las bacterias grampositivas
Complemento
Complemento C3b C3b Plasma Varias proteínas del complemento Superficies microbianas
Receptores Tipo Toll (TLR)
RECEPTORES TIPO TOLL (TLR) · Se conocen 10 TLRs · Están unidos a membrana
Reconocimiento de Patógenos por TLR
Bacterias grampositivas Bacterias gram- negativas Todas las bacterias con flagelos Lipopéptidos Peptidoglucano Lipopéptidos bacterianos bacteriano bacterianos LPS Flagelina bacteriana TLR1:TLR2 TLR2 TLR2:TLR6 TLR4 TLR5 Endosoma Membrana plasmática TLR3 Virus ARNbc ARNmc TLR7 ARNmc TLR8 TLR9 ADN CpG Virus, bacterias, hongos
Estructura del TLR
Estructura del TLR Repeticiones ricas en leucina Dominio TIR-
Activación de los TLR
RECEPTORES TIPO TOLL (TLR) · La activación de los TLRs da lugar a: · Inflamación (citocinas y quimiocinas) · Estado antivírico (interferones tipo I) · Estimulación de la inmunidad adaptativa
LPS Dominio TIR Dominio de muerte Proteína adapta- Idora Peptidoglucano TLR1, TLR2, TLR5, TLR6 TLR4 Membrana plasmática ADN CpG ARNbc MyD88 TRIF TLR7 TLR8 TLR3 TLR9 ARNmc Endosoma NF-KB IRFs DO Expresión de genes inflamatorios - Citocinas (TNF, IL-1, IL-6) Expresión de genes del interferón tipo | (IFN a/B) - Quimiocinas (CCL2, CXCL8, otras) - Moléculas de adhesión endotelial (selectina E) - Moléculas coestimuladoras (CD80, CD86) Secreción de IFN tipo | - Inflamación aguda Estado antivírico - Estimulación de inmunidad adaptativa
Receptores Tipo NOD (NLR)
RECEPTORES TIPO NOD (NLR) · NOD significa dominio de oligomerización de nucleótidos, también conocido como NACHT · Son los receptores que forman el INFLAMASOMA
Subfamilias de NLR
Subfamilia Ejemplos Estructura en dominios típica Activadores Función
NLRA
NLRA NLRA CARD TA NACHT LRA IFN-Y Expresión del MHC clase II
NLRB
NLRB NAIP Flagelina BIR NACHT LRR Generación en el inflamosoma de IL-1 e IL-18 activas; piroptosis (con NLRC4)
NLRC
NLRC NOD1, NOD2, NLRC3-5 CARD CARD NACHT LRR DAP (NOD1) Activación de NF-KB MDP (NOD2) Activación de NF-KB, autofagia, producción de interferón tipo l Flagelina, sistema Generación por el de secreción tipo III (NLRC4) inflamosoma de IL-1 e IL-18 activas; piroptosis
NLRP
NLRP NLRP 1-10 PYR NACHT LRR ATP extracelular, alumbre, asbesto, toxinas bacterianas, e IL-18 activas; piroptosis silice, ROS, K+ citosólico reducido (NLRP3) Lipopéptidos (NLRP7) Generación por el inflamosoma de IL-1 DAP: ácido diaminopimélico (derivado peptidoglicano de las gram - ) MDP: dipéptido de muramilo (derivado de peptidoglicano gram + y gram -)
Detectores de ADN Citosólico (CDS)
DETECTORES DE ADN CITOSÓLICO (CDS) · Son moléculas que detectan el ADN bicatenario (bc) en el citosol. · Inician respuestas antimicrobianas como la producción de IFN tipo I y la autofagia · La vía STING es una mecanismo importante de respuesta · AIM2 es otro detector de ADNbc que forma INFLAMASOMA
Mecanismo de Autofagia
La AUTOFAGIA es un mecanismo por el cual las células degradan sus propios orgánulos, como las mitocondrias, secuestrándolas dentro de vesículas rodeadas de membrana y fusionando las vesículas con los lisosomas. En la inmunidad innata, la autofagia es un mecanismo para llevar microbios citosólicos al lisosoma.
Vía STING y Respuesta a ADN
Retrovirus Transcripción inversa Virus de ADN ADN Bacteria GASc ADN propio ATP GTP di-GMPc 2'3'-GAMPc di-AMPc P IRF3 TBK1 STING PP IRF3 RE PP Transcripción del gen del IFN tipo I Inhibición de la replicación vírica Interferones tipo I
Detectores de ARN Citosólico Tipo RIG (RLR)
DETECTORES DE ARN CITOSÓLICO tipo RIG (RLR) · Reconocen ARNbc y dúplex ARN-ADN. · RIG-I y MDA5. · Están presenten en leucocitos y muchas células tisulares. · No solo inducen IFN tipo I, sino que también inhiben directamente la replicación de los virus al inhibir las interacciones entre el ARN y las proteínas.
Estructura de RIG-I
Basic inactive RIG-I Structure HELICASE DOMAIN CARD RO CARD C Basic active RIG-I Structure HELICASE DOMAIN GANA N CARD CARD S'PPP RD
Inflamasomas
CLPS/otros PAMP TLR ATP Membrana plasmática Flagelina Sistema de ADNbc PAMP DAMP Salida de K+ secreción tipo III LPS citoplásmico NLRP3 NLRC4 AIM2 Cristales ROS Procaspasa 4/5/11 NAIP5 ASC. Procaspasa 1 Caspasa 4/5/11 activa Transcripción del gen de pro-IL-1B y pro-IL-18 Inflamosomas Pro-IL1B Pro-IL18 Gasdermina D Núcleo Caspasa 1 (activa) Fragmento de gasdermina IL1B IL18 H2O Poros de doc gasdermina IL1B IL18 H2O Inflamación aguda Piroptosis Bacteria gramnegativa
Función de los Inflamasomas
INFLAMASOMAS Son complejos enzimáticos multiproteínicos que se forman en el citosol en respuesta a infecciones o lesiones celulares, que producen por mecanismos proteolíticos caspasa 1 activa y de esta forma generan formas biológicamente activas de las citocinas inflamatorias IL-1 e IL-18. Son responsables de las enfermedades autoinflamatorias CAPS (síndromes periódicos asociados a la criopirina [NRLP3])