Struttura degli acidi nucleici: DNA e RNA, topologia e replicazione
Slide di Università su Struttura Acidi nucleici. Il Pdf, un documento schematico di Biologia, illustra le componenti fondamentali di DNA e RNA, la topologia del DNA e il ruolo delle topoisomerasi, essenziali per la replicazione e trascrizione.
Mostra di più40 pagine
Visualizza gratis il Pdf completo
Registrati per accedere all’intero documento e trasformarlo con l’AI.
Anteprima
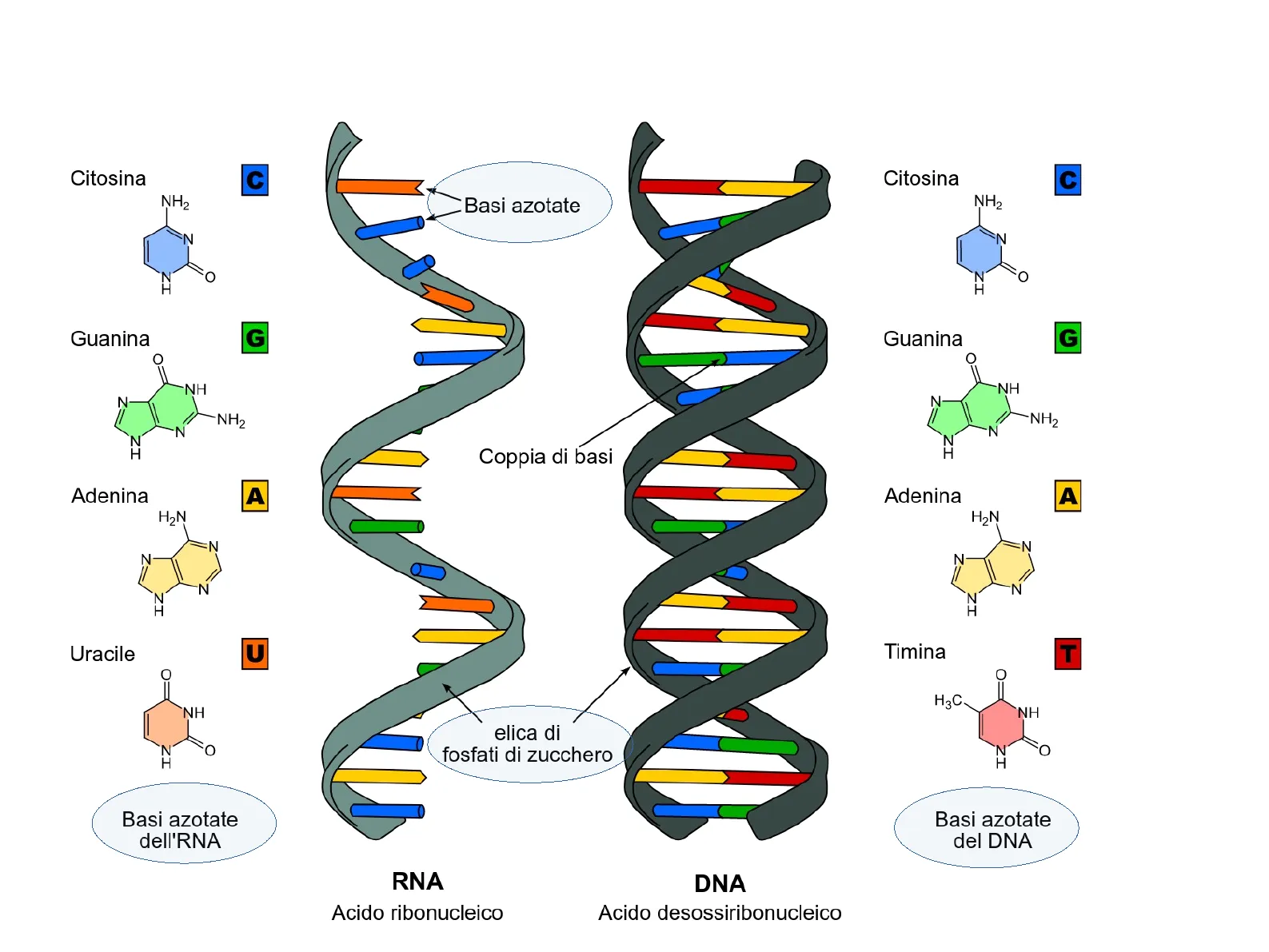
Struttura Acidi nucleici
Citosina C NH2 Basi azotate D Citosina C ŅH2 SN ZI Guanina G Guanina G O NH N NH2 N N H Adenina A H2N Z N N ZI Uracile U O NH ZI Basi azotate dell'RNA RNA Acido ribonucleico DNA Acido desossiribonucleico Adenina A H2N N N ZI Timina T H3C. NH ZI Basi azotate del DNA N NH N NH2 N ZI Coppia di basi elica di fosfati di zucchero
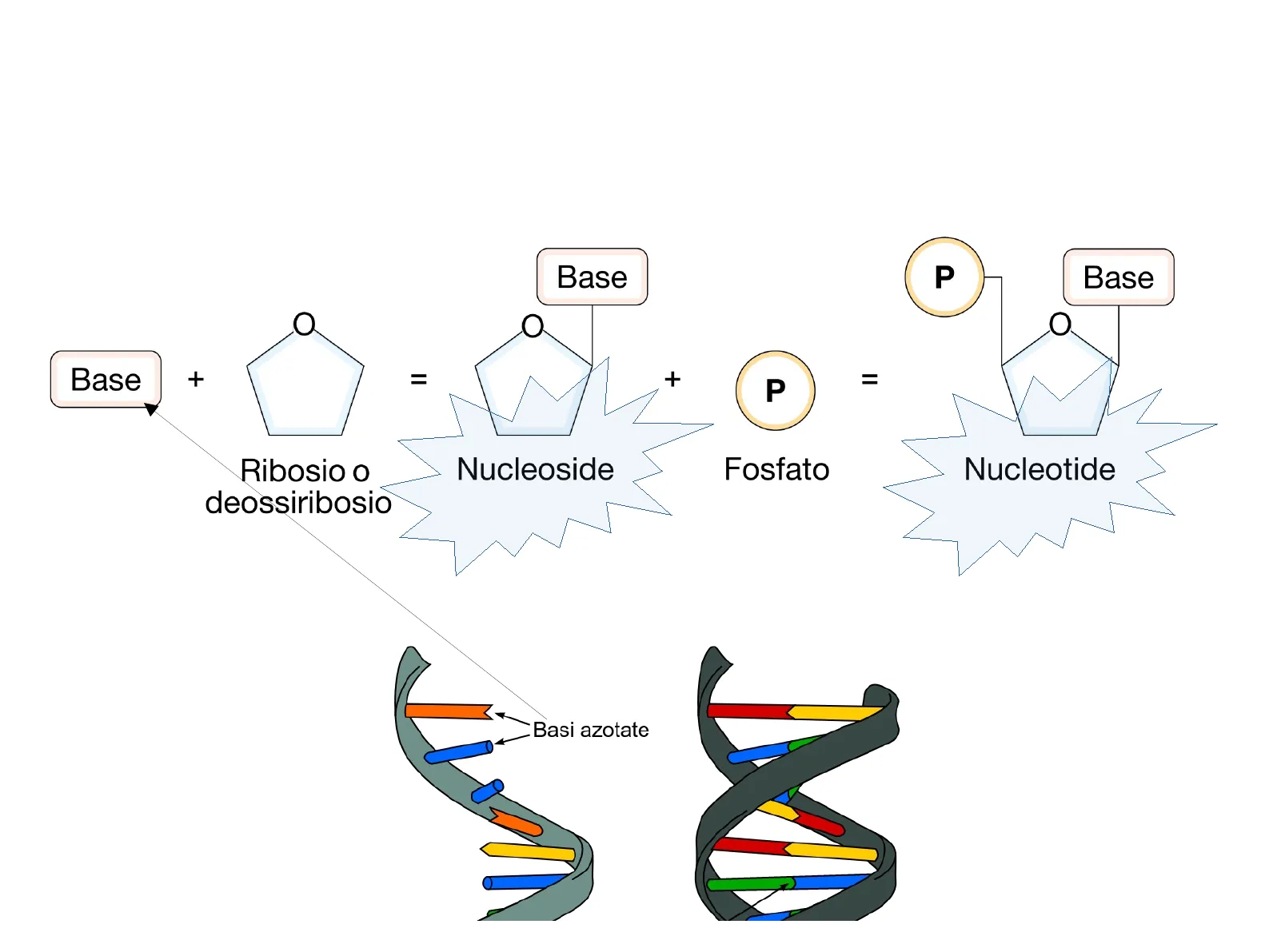
Struttura e Unità - nucleotidi
1Struttura Unità - nucleotidi Base P Base C Base + = + = P Ribosio o deossiribosio Nucleoside Fosfato Nucleotide RNA DNA Basi azotate
Termini ATP, ADP, AMP
2I termini ATP, ADP, AMP O O=2-0 II O ǁ I O P-O-CH2 O O γ β α g b a OH OH Ai nucleosidi possono essere legati uno o più gruppi fosfato prendono il nome di nucleotidi La presenza del residuo fosforico conferisce un carattere fortemente acido ai nucleotidi; i loro nomi alternativi per RNA sono acido adenilico, guanilico, citidilico e uridilico. Nel DNA i nucleotidi (desossinucleotidi) prendono il nome di acido desossiadenilico, desossiguanilico, desossicitidilico e acido desossitimidilico.
Struttura chimica degli acidi nucleici (DNA and RNA)
3struttura chimica degli acidi nucleici (DNA and RNA) catene polinucleotidiche I termini doppio anello eterociclico Purine Pirimidine C H CH3 4 N 5 3 2 6 1 O N H H H Uracile (U) 5 5 HO-CH2 OH HO-CH2 OH O O 4 1 4 1 3 2 3 2 OH OF OH H Ribosio Deossiribosio "OH" rende la molecola di RNA instabile H 4 N 5 3 2 6 1 O N I H H Adenina (A) Guanina (G) Singolo anello NH2 N 6 N 7 1 8 8 2 9 4 3 N N N H2N Timina (T) Citosina (C) H N 6 N 7 5 1 2 9 4 3 N O N 2 6 1 5 3 4 N NH2 5 49 I termini Poiché in ciascun nucleoside (sia lo zucchero che la base azotata) hanno una numerazione (1, 2, 3 ecc.) per indicare le varie posizioni della molecola, si usa aggiungere un apice [ ' ] alla numerazione relativa allo zucchero per distinguerla da quella della base.
Nucleotides
Nucleotides 0 O 5'eno P phosphate CH2OH 0-P-O-CH2 -6 O 0 1 NH, Al 5' 8 5 6 .0 9 4 IN base O OH OH OH 0-P=0 Coppia 0- 0 0= phosphate 0 NH, 6 I 5' 5 0 1 4º 2 sugar 1 3 2' 0 3'end OH (adenine) 3 N 2 2' 3'-monofosfato (Pirimidina) 5'-monofosfato (Purina) sugar 7 1 3' BN base (cytosine) 4
Polarità della catena polinucleotidica 5' -> 3'
4 5Polynucleotide chain Polarity 5' -> 3' important for all processes 5' O 1 NH2 "0-P=0 I I C Subunità nucleotidica 0 C N I HC CH 2 O C CH N O "0-P=0 H I- O C ,NH2 HC C Base pirimidinica 5' CH2 4' C 1' N N 3' 2' C O 0 O "0-P=0 C O C NH Base purinica CH2 O N N NH2 Conferisce assimmetria e polarità 0 1 "0-P=0 I O 3' 6 I Scheletro di zucchero-fosfato Legami fosfodiesterici 5'-3' O N HC NStruttura del DNA
Anni '50 e struttura del DNA
7Anni '50 3.4 Å A . . . T A ... TO destrorsa O C ... Gc A . . . To TO T. . . A C C ... G o O C . . . G M A . . . Tc O O G ... Cc T. . . Ac O O PC . . . G o CA .. . TSzo O DOUBLE HELIX. The two sugar-phos- phate backbones twist about on the out- side with the flat hydrogen-bonded base pairs forming the core. With these base pairs as the steps the structure resembles a helical staircase. Pauling Franklin Wilkins | diffrazione raggi X| STESSA QUANTITÀ G-C così A-T Nature April 25th 1953 53' 5' Legame idrogeno (H) Base Impalcatura zucchero-fosfato · A-T -> 2 legami H · G-C - 3 legami H Catene ANTIPARALLELE 5', 3 Asimmetria dell'elica H / N H 4 C N 3 2 N 6 H 1N G N 2 O Zucchero N H N Zucchero 9 1 giro d'elica = 34 A = ~ 10,5 paia di basi Adenina Guanina Citosina Timina 3' 5' 20 Å (2 nm) O T N3' 5' Legame idrogeno 1 giro d'elica = 34 Å = ~ 10,5 paia di basi .. .- Base Impalcatura zucchero-fosfato .. Adenina C Guanina C Citosina C Timina Solco maggiore H H A N A 1 1 O 4 N. Z 7 2 -N N G N 3 2 O N HI dR dR A 1 H D Gruppi chimici: D - Donatori di legami H A > Accettori di legami H D H non polari D O-I H CH3 O H N 4 T - N 6 2 -N N 2 .O. N dR dR H A A H Solco minore 5' 1 H O O - N N CH3 O C 3' N T N HO N H O 1 CH2 N - . H O N IN P HI N O G N N H N O O CH3 CH2 H H H N N N a N C A N O N H O P CH2 I O N- O O O P C H -N G CH2 N O H H OH Solco maggiore CH2 appaiamento 0 P O 5' I A 3 O 3' 5' 20 Å (2 nm) P- 0- 1 - HI A CH2 -N O p- O O O 1 C CH2 0 O T II CH2 H N 5 C 6 O C N +4 Solco minore -N 3' M A 10 N H 1 5 ISolco minore 12 Å (1,2 nm) - giro completo 34Å (10nt) · distanza tra 2 nt 3,4Å 22 Å (2,2 nm) L · diametro 20Å Solco maggiore Importante per l'interazione con le proteine(alfa elica) a-elica H O C nei fosfati della catena fosfodiesterica Ce N nelle basi P X Solco minore Solco maggiore
Comportamento degli acidi nucleici in soluzione acquosa
11COME SI COMPORTANO GLI ACIDI NUCLEICI In soluzione acquosa: · idrofilica -, scheletro zucchero-fosfato · Idrofobica - basi Propensione delle due emi-eliche a stare insieme dipende da varie forze: · Legami H · Idrofilica e idrofobica · Impilamento Mantenimento minimo di contatto con l'acqua La stabilità del DNA in soluzione dipende dallacomposizione delle basi (se ricco di G-C ha 3 legami H -> più stabile) 0,34 nm 3,4 nm Impilamento delle basi.
Forme del DNA: A, B, Z
12DNA B DNA A DNA Z 0,34 nm 3.4 mm Se si riduce l'umidità relativa il DNA assume la forma A, che è destrorsa come la forma B, ma: le coppie di basi presentano una maggiore angolatura rispetto al piano perpendicolare all'asse della doppia elica; . ci sono 11 coppie di basi per ogni giro di elica; · il passo dell'elica è di 25 Å (34) e il diametro è di 23 Å (20), una forma "tarchiata" rispetto alla forma B. forma A Presente in vivo, quindi in soluzione acquosa: per duplex, formati da 2 filamenti di RNA oppure da un filamento di DNA e uno di RNA. forma Z (più particolare). Caratteristica peculiare - elica sinistrorsa (in specifici tratti con proteine legate)
Coesistenza di tratti DNA B e DNA Z
13DNA B DNA Z DNA B XXX DNA Z DNA B Estrusione timina Estrusione adenina Giunzione B-Z Nella stessa molecola di DNA possono coesistere tratti di DNA B e di DNA Z.
Altre conformazioni del DNA
14Altre conformazioni del DNA Le conformazioni che assume sono importanti per la funzione e le strutture che va a formare
Quartetto di G
15quartetto di G Loop 1 Loop 2 Loop 3 5'-AGGGTTAGGGTTAGGGTTAGGG-3' Chromosome 3' O 3' 5' 5' Telomere Repeats TTAGGGTTAGGGTTAAGGGTTAGGGTTAGGGTTAGG 3' AATCCCAATCCCAATCCC 5' 16A B H dR I 1 C 4 T T A A G G G G G G G G G T A A 5' 3 c - = 3 3 3' 3' 3 5' 5 5' 5 5' Quartetto di G intermolecolare Il quartetto di G. (A) Struttura di un DNA (o RNA) quadruplex che si può formare tra 4 tratti a singolo filamento che contengano 3 o più G. (B) Struttura chimica del quartetto di G; le linee tratteggiate indicano i legami idrogeno degli appaiamenti di tipo Hoogsteen. (C) Esempi di diversa disposizione dei filamenti: intramolecolari, intermolecolari (2 o 4 filamenti) e con orientamenti 5' -> 3' che possono essere 2 a 2 antiparalleli o tutti con la stessa direzione. (a) 5' 5 Higher-order DNA G-quadruplex 3' Y 3' DNA-RNA G-quadruplex RNA G-quadruplex - H -N 1 H H-N H N H N N N N N- dR N N N / dR H 3' 5 Quartetto di G tipo "basket" intramolecolare -N N N dR N N -N -N H N O O N-N A 5 3' Quartetto di G tipo "basket" intermolecolare
Conformazioni del DNA: sequenze palindromiche e strutture cruciformi
17Altre conformazioni 5' TGCGATATCGCA. 3' A 3' · ACGCTATAGCGT 5 Seq palindromica: 2 seq ripetute e adiacenti B 5' TGCGATACTCATCGCA 3' 3' · ACGCTATGAGTAGCGT 5' C. T A C T A A T G C C G G C T 5' 3' 3' 5' A C G C C G T A A T T G (mn S) Å OS iasd ib sisq 2, 01- = ÅAC = soile'b ovip I sninebA 0 sninsu? snizotio snimiT 000 -- 3. G A Sequenze ripetute e invertite separate da una seq breve 3. siutsolsqml Struttura cruciforme causata da una seq ripetuta e invertita che si è APPAIATA
Struttura a forcina dell'RNA
185' UGCGAUACUCAUCGCA . 3' Ansa terminale C U A C RNA U A U Stelo G C C G G C U A 5' . 3' Figura 2.27 Struttura a forcina.
DNA intrinsecamente curvo
19DNA intrinsecamente curvo A B C T (A) Struttura regolare di una molecola duplex di DNA secondo il modello di Watson e Crick. T (B) Alcune coppie di basi adiacenti ( es. A-T/A-T), non essendo perfettamente parallele, introducono piccoli piegamenti della molecola duplex; T se tali perturbazioni sono distribuite in maniera casuale lungo la molecola di DNA, risultano in una struttura un po' irregolare ma sostanzialmente dritta. (C) Se la sequenza nucleotidica è tale per cui i piccoli angoli tra le coppie di basi adiacenti si ripetono regolarmente a ogni giro di elica (es ogni 10 pb), gli angoli si sommano tra loro e risultano in una curvatura intrinseca della molecola di DNA. Sono forme spesso con proprietà strutturali e funzionali essendo presenti in vivo
Topologia del DNA e DNA topoisomerasi
20Topologia del DNA e DNA topoisomerasi (enzimi) TOPOLOGIA studio delle proprietà geometriche delle figure che non dipendono dalla nozione di misura, ma sono legate a problemi di deformazione delle figure stesse ENZIMA Sostanza di natura proteica che ha proprietà di accelerare una reazione chimica specifica senza esser consumata e senza entrare nei prodotti finali della reazione.
Vantaggi e problemi della doppia elica
21Doppia elica - molti vantaggi: - stabile - quindi può proteggere la conservazione dell'informazione genetica - possibilità di correggere errori e rotture grazie alla complementarietà Ma pone problemi da superare nella trascrizione e replicazione Le strutture topologiche se non controllate possono interferire con l'espressione genica, la duplicazione del DNA, la segregazione dei cromosomi. (a DNA circolare rilassato e superavvolto. P. (b)
Superavvolgimenti nella replicazione e trascrizione del DNA
22Replicazione Precatenazione (+) superavvolgimento Trascrizione (-) superavvolgimento (+) superavvolgimento Figura 2.42 La replicazione e la trascrizione del DNA generano superavvolgimenti della doppia elica.
Transizioni strutturali del DNA indotte dall'energia libera
23A B Separazione dei filamenti (denaturazione di regioni ricche in A+T) Struttura Z (in corrispondenza di regioni di alternanza Pu/Py) CT A )c T A A T G C C G G C T A 5' 3' 3 5' A T G G C C G T A A T T G GA L'energia libera contenuta in una molecola superavvolta può indurre transizioni strutturali del DNA. D C Strutture cruciformi (in corrispondenza di palindromi) . . .
Controllo dello stato topologico del DNA
25· Le strutture topologiche se non controllate possono interferire con l'espressione genica, la duplicazione del DNA, la segregazione dei cromosomi. · Lo stato topologico del DNA deve essere tenuto sotto CONTROLLO · la doppia elica DEVE essere aperta e richiusa TEMPORANEAMENTE
DNA TOPOISOMERASI e superavvolgimenti
27DNA TOPOISOMERASI gli Enzimi che controllano questa funzione sono le Catalizzatori dei processi biologici tagliano il DNA su UNO o ENTRAMBI i filamenti (controllano il superavvolgimento) Superavvolgimenti (stato topologico sotto controllo) - contiene energia 5 3 ...- 3' 5' 28