Costituenti cellulari: aminoacidi, proteine, acidi nucleici, lipidi e carboidrati
Slide dall'Università sui costituenti cellulari: aminoacidi e proteine, acidi nucleici, lipidi e carboidrati. Il Pdf esplora la struttura del DNA, inclusi i tre isomeri della doppia elica (A, B, Z form), e il processo di denaturazione, sia fisiologico che in laboratorio, per studenti di Biologia.
Mostra di più41 pagine

Visualizza gratis il Pdf completo
Registrati per accedere all’intero documento e trasformarlo con l’AI.
Anteprima
Costituenti Cellulari e DNA
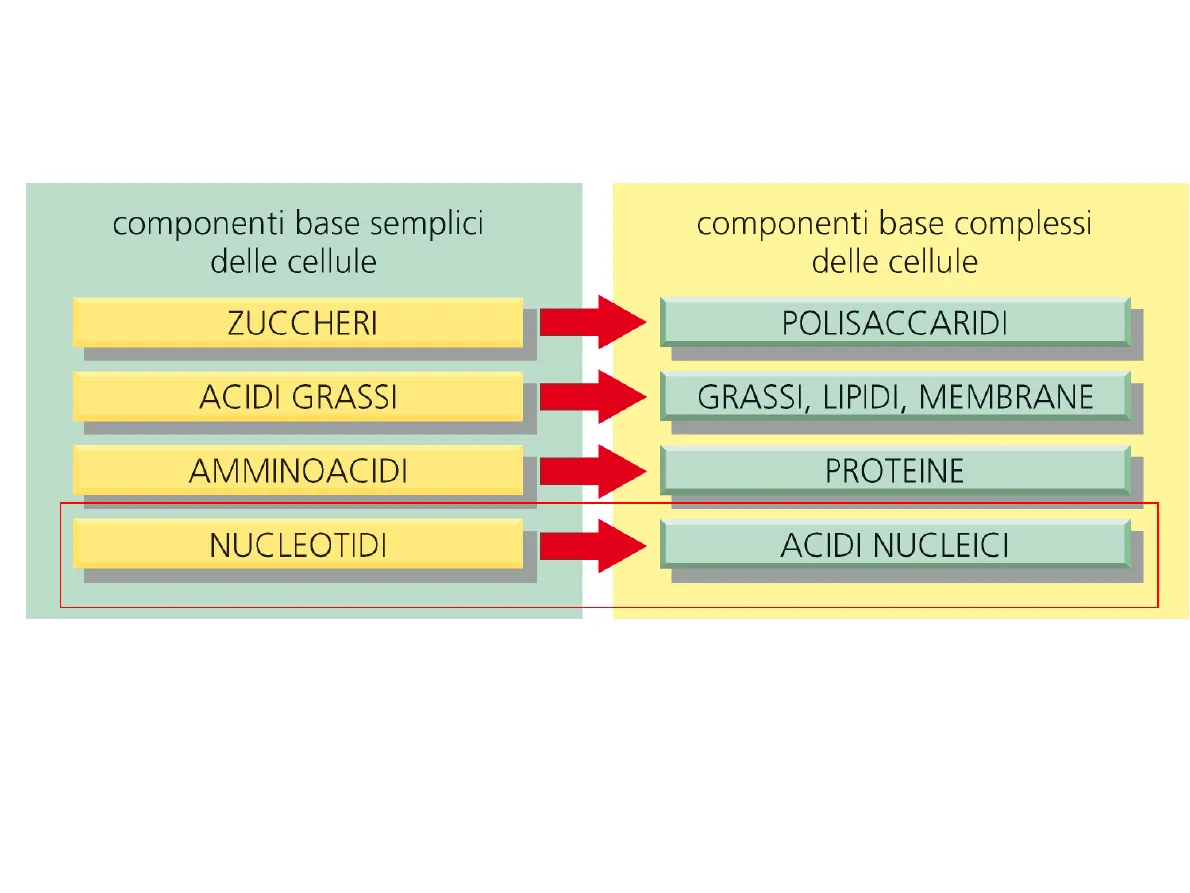
Costituenti cellulari: aminoacidi e proteine; acidi
nucleici; lipidi semplici e complessi; carboidrati.componenti base semplici
delle cellule
Componenti Base Semplici delle Cellule
ZUCCHERI
ACIDI GRASSI
GRASSI, LIPIDI, MEMBRANE
PROTEINE
NUCLEOTIDI
componenti base complessi
delle cellule
POLISACCARIDI
AMMINOACIDI
ACIDI NUCLEICIDNA è la macromolecola biologica depositaria
dell'informazione genetica
Descrizione della Struttura a Doppia Elica del DNA
Descrizione della struttura a doppia elica del DNA
da parte di James Watson e Francis Crick
A Structure for Deoxyribose Nucleic
Acid
Watson J.D. and Crick F.H.C.
Nature 171, 737-738 (1953)
April 25, 1953: James Watson and Francis Crick's classic paper
that first describes the double helical structure of DNA. With
some understatement they note that the structure "suggests a
possible copying mechanism for the genetic material".IL DNA E' IL MATERIALE GENETICO UNIVERSALE
Il DNA come Materiale Genetico Universale
Prima Prova: Trasformazione Batterica (1928, Griffith)
PRIMA PROVA
TRASFORMAZIONE BATTERICA:(1928, Griffith)
SECONDA PROVA
IL DNA PUO' ESSERE TRASFERITO DA UNA SPECIE
ALL'ALTRA E RESTARE COMUNQUE FUNZIONALE
TERZA PROVA
LE CELLULE POSSONO ACQUISIRE UNA FUNZIONE NUOVA
IN SEGUITO ALLA TRASFEZIONE DI DNA DI ORIGINE
ESOGENAPRIMA PROVA
TRASFORMAZIONE BATTERICA:(1928, Griffith)
Tipi di pneumococco
Iniezione delle cellule
Risultato
Capsula
dall'aspetto liscio
(S, smooth)
S vivo
Muore
S ucciso
con il calore
Vive
R vivo
Vive
Assenza
della capsula,
aspetto ruvido
(R, rough)
S ucciso
con il calore
R vivo
Muore
I batteri virulenti recuperati dall'infezione mista avevano il rivestimento liscio ti
tipo III.
Conclusione: alcune proprietà dei batteri S morti di tipo III avevano trasformato
i batteri R vivi di tipo II tanto da farli diventare capaci di produrre il
polisaccaride capsulare di tipo III e diventare virulenti.
Seconda Prova: Trasferimento del DNA tra Specie
SECONDA PROVA
IL DNA PUO'
ESSERE
TRASFERITO DA
UNA SPECIE
ALL'ALTRA E
RESTARE
COMUNQUE
FUNZIONALE
Esperimento che
identifica l'agente in
grado di trasformare i
batteri.
Topo iniettato
con i batteri S
uccisi con il calore
e i batteri vivi R
Batteri S vivi
isolati dal topo morto
Estrazione
del DNA
Trasformazione
Batteri R
Batteri S
Terza Prova: Acquisizione di Nuove Funzioni tramite Trasfezione di DNA
TERZA PROVA
Cellule prive del gene TK non possono produrre
la timidina chinasi e quindi muoiono in assenza di timidina
IL DNA è il materiale
genetico delle cellule
e puo' essere trasferito in
altre cellule per introdurre
nuove caratteristiche
Cellule morte
Aggiunta del DNA TK+
Cellule vive
Colonie
di cellule TK+
Alcune cellule assumono il gene TK; la progenie delle cellule
trasfettate si addensa e forma una colonia
Il DNA come Materiale Genetico dei Virus
TERZA PROVA
IL DNA E' IL
MATERIALE
GENETICO DEI
VIRUS
Solo il DNA marcato (e non
le proteine) è trasmesso alla
progenie fagica prodotta
infettando dei batteri
Infezione batterica con i fagi
marcati
32P nel DNA
I
35S nelle proteine
Separazione degli involucri
fagici dai batteri infettati
S
I batteri
infettati
contengono
il 70% della
marcatura
con 32P
Gli involucri dei fagi
contengono l'80%
della marcatura
con 35S
Isolamento
delle particelle
fagiche figlie
I fagi figli
hanno il 30%
del 32P usato
per marcare
e meno
dell'1%
del 35S
Struttura e Componenti degli Acidi Nucleici
I Nucleotidi: Subunità degli Acidi Nucleici
· I nucleotidi sono le
subunità (monomeri) degli
acidi nucleici
estremità 5'
I
"0-P=0
N
NH
I
5'CH2
0
N
N
NH2
4'
1º
3'
2'
O
-
"O-P == O
NH2
1-0-
N
N
CH2 O
N
N
O
"0-P=0
1
H3C
NH
T
CH2 O
N
0
O
"0-P=0
NH2
0
N
1
5'CH2 O
N
4'
1'
3'
2'
0
estremità 3'
A
O~
O=P-O-
H-
N
NH2
C
C
1
O=P-O
N
C
O
O=P-O
- CH2
O
N
C
CH
H
H
OH OH
trifosfato
ribosio
adenina
adenosina
(A)
(B)
O
1
2
C
C
G
Monosaccaridi degli Acidi Nucleici
Monosaccaridi degli Acidi Nucleici
-2-deossi-D-
ribosio (DNA)
5
HO-CH2
0
OH
1
H
H
H
2
T'ossidrile sul C-2
OH H
2-deossi-D-ribosio
-D-ribosio (RNA)
5
HOCH2
O
OH
1
4
H
H
H
3
2
H
OH OH
D-ribosio
Basi Azotate degli Acidi Nucleici
Basi AZOTATE degli acidi nucleici
Le basi azotate presenti negli acidi nucleici
appartengono a due classi:
NH2
CH
N
N
Nº
C
CH
HC
NH
H2N
N
Z-x
PURI
NE
ADEN
GUAN
C
NH2
H
CH3
CH
Nº
CH
HC
CH
0
I
I
N
X
dX
PIRIMI
DINE
URA
CILE
TIMI
NA
H
N
N
Z-X
A
H
0
N
0
X
CITOS
INA
Nucleosidi e loro Caratteristiche
Nucleosidi
Il legame tra basi azotate e ribosio forma i
•
Nucleosidi
· Il legame è di tipo b-N-glicosidico tra il
Carbonio anomerico del ribosio e l'N 9 delle
purine o N1 delle pirimidine
· Il legame può avere due orientazioni: Syn e
Anti. Anti è predominante
· Hanno numerosi gruppi polari e sono solubili in
acqua.
· Sono facilmente idrolizzabili da soluzione acquose
di acidi.
NH2
N
Z
1
Z
N
HO
syn
OH OH
NH2
N
N
0
i
HO
OH OH
Nucleotidi: Esteri Fosfato dei Nucleosidi
Nucleotidi
· I nucleotidi sono ESTERI FOSFATO dei nucleosidi.
· Il sito di fosforilazione è spesso l' ossidrile al 5' del ribosio
· Possono essere mono- di- e tri-fosfati (Es .: TMP, TDP, TTP.)
· I di- e tri-fosfati sono legati da legame anidridico, stabile e ad
alta energia
Ester
0-
0-P-O-P-O-P-O-CH2
Adenine
O
Ö
Ö
Ö
H
H
Anhydride
H
H
Anhydride
OH OH
ATP
Acidi Nucleici: Formazione e Legame Fosfodiesterico
Acidi Nucleici
· Gli acidi nucleici (polinucleotidi) si formano dalla
condensazione di due o più nucleotidi tra il fosfato
legato al 5'-OH del ribosio di un nucleotide ed il 3'-OH del ribosio
dell'altro con eliminazione di H2O
· Il legame fosfodiesterico è direzionale, e la sequenza va da
5°
3
Estremità 5'
H
N
OH O
=0
OH
C
H
HO-P-O-P-O-P-O.
OH O
5'
N
-2
H
13º
H
H
0
H
HO-P=0
=
N
HA
fosfodiesterico
0
5'
H
CH2
CH2
13º
HO
H
H
OH
0
OH
HC
HO-P-O-P-O-P-O
H
OH
Ö
5
O
Pirofosfato
4CH
H
H
.C'2.F
Deossiribosio
I
HÒ
1
3
HO
H
Estremità 3'
0
H
Legame/
HO-P=0
N
HC
0
5'
N
Nº
H
3'
H
N
HO-P=0
OH 0
HC
HO-P-O-P-OH
H
=0
CH2
CH2
H
H
13
HC
QH º QH
H
5'
Q=0
-CH2
N
-CH2
HO-P-O-P-O-P-O.
ÒH Ö
Z-I
H
H
2
N
I OH
HA
Formazione del Legame Fosfodiestere del DNA
Formazione del legame fosfodiestere
del DNA
La reazione avviene per
un attacco nucleofilo
da parte del gruppo
ossidrile 3' del
nucleotide all'atomo di
fosforo a di un
nucleoside 5'-
trifosfato, causando il
rilascio del pirofosfato
e la formazione del
legame. Tale reazione
in vivo è catalizzata
dalla DNA polimerasi
1
0
1
HỌC
O
Base
...
I
H
H
H
HQ
H
1
0
O
0
0-P-O-P-O-P
1
o-
0
0
H2C
O
Base
...
H
H
V
L
H
HO
H
Legame
fosfodiestere
Polimerizzazione 5' a 3' dei NTPs
H5' to 3' polimerizzazione dei NTPs
dNMP
O
base
O
5' end of chain
base
5'
"O-P-O-CH2
1
.O
"O-P-O-CH2
I
-O
O
sugar
OH
+
"O-P=0
1
base
O
base
TO-P-O-CH2
O
0-
sugar
Legame
fosfodiestere
sugar
3' OH
3' end of chain
OH
sugar
3'
O
-DNA
5' End
0-A-0-
A
5' CH2
O
H
H
H
H
3'
O
H
O
OH
O-P=0
Ò
G
-
O
H
H
H
H
3
3'
O
H
O
OH
O-P=O
0-P=O
O
C
5' CH2
O
H
H
H
H
3"
3'
O
H
O
OH
O-P=0
O-P=O
1
O
A
5' CH2
O
H
H
H
H
3'
O
H
O
OH
H
Ħ
3' End
3' End
RNA
5' End
O
O-P=O
-A-0-
U
5' CH2
O
H
H
H
H
3'
Phosphodiester
linkage
O-P=O
O
T
5' CH2
O
5' CH2
H
H
H
H
in io
O
G
5'CH2
O
H
H
3
-O-
O
C
A
5' CH2
O
H
H
H
H
3'
H
H
3'
Ò
Gli acidi
nucleici hanno
una struttura
ripetitiva
O-P=ONH2
7
6
N
5
N 1 adenine
•
the 5' end wQ 5'
8
9
CH2
N
4
~N
0-
ACIDO
DEOSSIRIBONUCLEICO
(DNA)
0
7
6
5
IN~H
8
guanine
9
3
N
4
NH2
-H
H-
3'
2
0
H
H
4
0
OH
5
N-H
0=P-0
1
5
I
CH2
00
0-
H
H
1'
3'
2'
4
3
0
OH
1
2 cytosine
6
1
5
I
CH2
00
4'
1
3'
2'
H
H
0
OH
0=P-0
the 3' end
00
A Section of
a RNA Chain
Note:
· the sugar is ribose
. uracil replaces thymine
ACIDO
RIBONUCLEICO
(RNA)
4
thymine
H2
CH3.
N-H
3
O=P-O
5'
6
1
2
0
00
-0-
H
1'
3'
2'
H
H
H2
0
0=P-OL
the 3' end
1
0
4
NH2
H
H
5
N
O=P-0
N
0
3
D-
2
uracil
6
~12
CH2
4'
A Section of
a DNA Chain
CH2
N
4'
C
00
0-
4'
1'
3'
2'
C H
0
5
the 5' end ~0 5'
5
3
cytosine
0
N
2
O=P-O
6
1
-
N
0
CH2
NH2
3
2'
H
C H
4
H2
1'
3
2
·H
4
5'
HNH2
N
N
HN
H2N
N
0-
O
0-P-O-CH2_O
Ö
H
0-P-O-CH2_O
Ö
H
H
H
OH
Ħ
Deoxycytidylate
(deoxycytidine
5'-monophosphate)
C, dC, dCMP
Deoxycytidine
NH2
N
N
0-P-O-CH2_O.
Ö
H
H
Ħ
H
OH
OH
Cytidylate (cytidine
5'-monophosphate)
Symbols:
Nucleoside:
A, AMP
Adenosine
O
N
HN
HN
H2N
N
O
O
"O-P-O-CH2
Ö
O
Ö
H
H
H
H
H
H
OH
OH
Uridylate (uridine
5'-monophosphate)
U, UMP
Uridine
NH2
CH3
HN
N
N
N
0-P-O-CH2
O
"0-P-O-CH2_0
Ö
H
H
H
H
OH
H
Nucleotide:
Deoxyadenylate
(deoxyadenosine
5'-monophosphate)
Deoxyguanylate
(deoxyguanosine
5'-monophosphate)
Deoxythymidylate
(deoxythymidine
5'-monophosphate)
G, dG, dGMP
Deoxyguanosine
T, dT, dTMP
Deoxythymidine
(a) Deoxyribonucleotides
NH2
N
N
N
N
O
-
"O-P-O-CH2
0
Ő
H
H
H
H
H
H
OH
OH
OH
ỞH
Nucleotide: Adenylate (adenosine
5'-monophosphate)
Guanylate (guanosine
5'-monophosphate)
G, GMP
Guanosine
(b) Ribonucleotides
C, CMP
Cytidine
Symbols:
Nucleoside:
A, dA, dAMP
Deoxyadenosine
H
H
H
H
OH H
OH
Ħ
O
N
N
N
N
H
H
H
N
N
"0-P-O-CH2
.OLex. 4
Il DNA: Struttura Primaria e Secondaria
Struttura Primaria del DNA
Il DNA
Deossinucleotidi concatenati
tramite legame fosfodiestereo
· La sequenza delle basi in
direzione 5'
3' determina la
struttura PRIMARIA
· L'uracile non è mai presente nel
DNA, mentre la Timidina è
specifica.
· Presenza di basi modificate
(metil-citosina)
Struttura Secondaria del DNA: Modello Watson-Crick
STRUTTURA SECONDARIA DEL DNA MODELLO
WATSON-CRICK
· Elica destrorsa costituita da due
catene polinucleotidiche
antiparallele
· Le basi sono disposte all'interno
dell'etica allineate ad angolo retto
con l'asse dell'elica (deossiribosio
e fosfato all'esterno)
· Le due catene sono unite da
legami idrogeno tra purine di una
catena e pirimidine dell'altra
catena
➢
G-C formano 3 legami idrogeno
➢
A-T formano 2 legami idrogeno
(A)
elementi costitutivi del DNA
zucchero
fosfato
+
G
G
zucchero
fosfato
base
nucleotide
(C) DNA a doppio filamento
3'
5'
CE
G
A
T
T
A
T
A
G
U
G
C
ossatura
zucchero-fosfato
CE
G
C
G
C
G
A
A
.
G
= C
O
T =
A
5'
3'
coppie di basi unite
da legami a idrogeno
(B)
filamento di DNA
5'
3'
G
C
A
(D)
DNA a doppia elica
3'
5'
G
C
T
A
A
T
A
G
A
T
5'
3'
T
G
Doppia Elica del DNA
5'end
Doppia elica
3'end
3'end
5'end
Accoppiamento delle Basi nel DNA
Accoppiamento delle basi
Hydrogen Bonded Base Pairs
H
H
N
N-
-H ----
CH3
N
N-H ----- N
Sugar
N=
N
N-H ----- O
Sugar
H
GC
A === T
H
N-H ---- O
CH3
N ---- H-N
N
N
N
=N
5
NHI-H
H
MI
H
cytidine : thymidine
H
O ---- - H-N
N
N.
N
N-H ---- N
Sugar
Sugar
Sugar
Sugar
Sugar
N
N
0
Sugar
guanosine : adenosine
Unfavorable Interactions
N
O ----- H-N
N ----- H-NCH3
5'
3'
H
HILO
C
H
N
-3.0 Å->
Thymine
C
G
N
C
H-N
N
11
N
H-C
C-1'
1
Ö
N
C
N
H
C-1'
11.1 Å
H
H
1
1
C
C
H
₭-3.0 Å->
Cytosine
N
C
N
C-
N-HININ
C-1'
1
C
C
N
N
C-1'
A
C
G
A
T
3'
5'
COPPIE DI BASI COMPLEMENTARI A-T
G-C
appaiamenti diversi sono sfavoriti poiché non si formano legami ad
idrogeno
Adenine
-C
A
T
A
T
T
A
Guanine
G
C
N-HILO
-2.9 Å->|
HÍ
10.8 Å-
k-2.8 Å->
C
1
C
O INI H-N
₭-2.9 Å->
H-C
T(a)
Struttura del DNA e Rotazione delle Basi
STRUTTURA DEL DNA
Ogni coppia di basi è ruotata
di circa 36° intorno all'asse
dell'elica rispetto alla coppia
di basi successive
Pertanto un giro completo
di elica di 360°si compie
ogni 10 coppie di basi.
Minor
groove
Major
groove
Normal B DNA