SiRNA (Small Interfering RNA): meccanismo di RNA interference e silenziamento genico
Documento di Appunti sull'siRNA (Small Interfering RNA), il meccanismo di RNA interference e il silenziamento genico. Il Pdf, utile per studenti universitari di Biologia, descrive le tecniche di laboratorio per l'analisi dei miRNA, come la Real-time PCR e l'ibridazione in situ, e le metodologie per l'identificazione dei target dei miRNA.
Mostra di più13 pagine
Visualizza gratis il Pdf completo
Registrati per accedere all’intero documento e trasformarlo con l’AI.
Anteprima
Introduzione all'RNA Interference
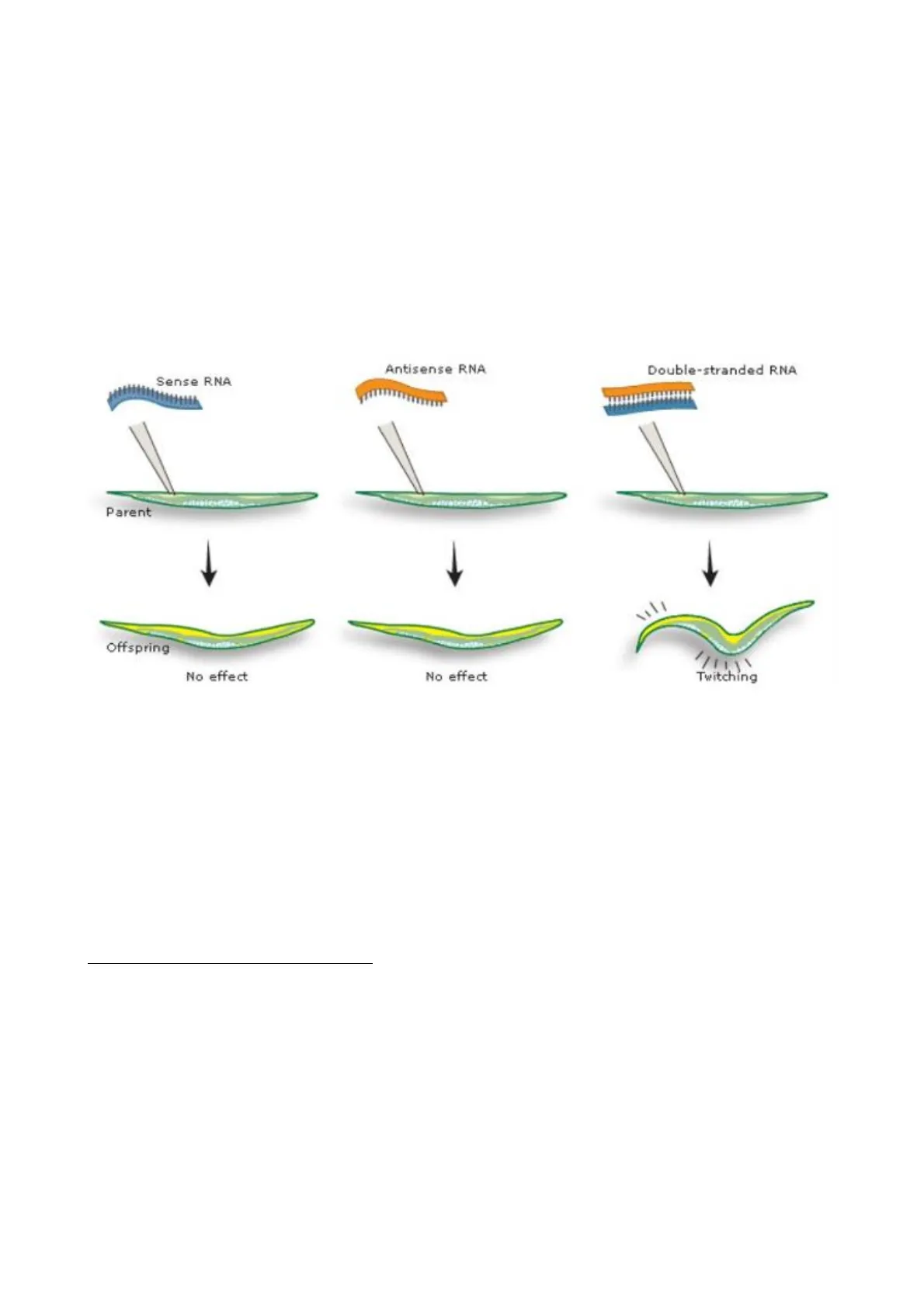
Lorenzo Del Prete Nel 2006 Andrew Fire e Craig Mello hanno vinto il premio Nobel per la scoperta dell'RNA interference, cioè del silenziamento genico mediato da piccoli RNA a doppio filamento. Lavorando sul verme nematode C. Elegans, iniettarono RNA corrispondente al messaggero di un gene codificante per una proteina fondamentale per la funzione muscolare in C. elegans. L'iniezione di RNA a singolo filamento (sia senso che antisenso) non aveva effetti sulla funzione muscolare; invece, l'RNA a doppio filamento causava la contrazione del C. elegans in modo del tutto analogo alla perdita di funzione della proteina. L'espressione della proteina causava quindi il fenotipo normale del verme, in caso contrario invece, il verme presentava contrazioni spontanee, cosiddetto "twitching". Questo fenomeno di interferenza a RNA su una sequenza specifica di un gene viene chiamato "RNA interference".
Sense RNA Parent Offspring No effect Antisense RNA Double-stranded RNA Twitching
Definizioni Chiave
Diamo qualche definizione:
- Per Silenziamento genico (Knock down), si intende inibire l'espressione di un gene specifico;
- Con il termine invece "siRNA" (small interfering RNA, piccoli RNA interferenti), intendiamo un
processo naturale che serve a regolare l'espressione genica; la cellula esprime degli ncRNA (RNA
non-codificanti) e tra questi ci sono anche i precursori degli siRNA, i quali vengono processati
all'interno del nucleo della cellula, fino a generare due classi di piccoli RNA, con dimensioni comprese
tra i 20-30 nucleotidi a doppio filamento:
- siRNA (small interfering RNA)
- miRNA(microRNA)
Funzionamento delle Molecole siRNA e miRNA
Come funzionano entrambe le molecole? Dell'RNA a doppio filamento, solo uno dei due filamenti si va ad appaiare ad un messaggero bersaglio; una volta appaiato avviene, o la degradazione del messaggero bersaglio, oppure viene inibita la traduzione di quel messaggero quando esso è già legato ai ribosomi (inibita la sintesi proteica). Il siRNA è un meccanismo che le cellule hanno evoluto per difesa contro le infezioni gravi; sia le piante che i funghi hanno iniziato a produrre queste molecole per inibire la replicazione e la diffusione del virus. Questa è considerata la prima forma evolutasi di sistema immunitario di un essere vivente.
Scoperta e Origine dei siRNA
Nelle piante sono stati scoperti in maniera casuale cercando di produrre delle piante transgeniche; un esempio è stato quello di introdurre nella petunia il transgene della Calcone sintasi (che regola la pigmentazione dei petali delle petunie) per aumentare la colorazione dei fiori (volevano che fosse più viola). Invece a seguito dell'iniezione si ottenne il risultato esattamente opposto, ottenendo un fiore quasi completamente bianco; maggiore era l'iniezione del transgene, più comportava perdita di colorazione. > Esisteva qualcosa nella pianta che impediva l'espressione del transgene, operando come meccanismo di difesa contro un agente No effectesterno. Successivamente si è osservato che l'RNAi è un meccanismo di regolazione dell'espressione genica a livello post-trascrizionale presente in molti organismi e tipi cellulari ed è mediato da piccole molecole di RNA (siRNA). I siRNA possono avere origine sia endogena che esogena:
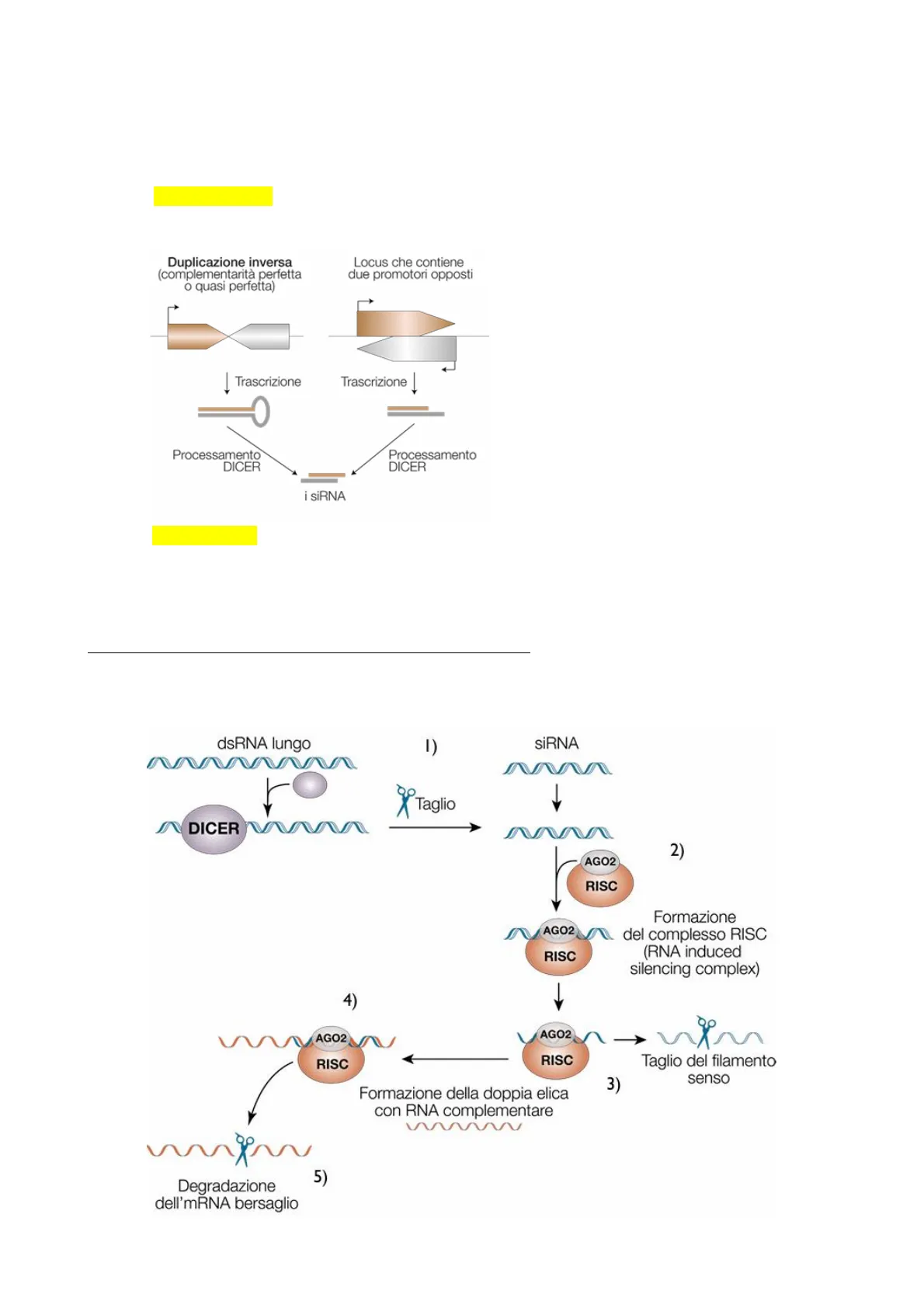
- i siRNA endogeni ("endo siRNA") sono trascritti da geni nucleari della cellula stessa; servono per alcune funzioni specifiche come il ciclo cellulare o geni specializzati nel differenziamento di un particolare tessuto. I siRNA endogeni derivano dalla trascrizione di regioni ripetute del genoma (ad Duplicazione inversa (complementarità perfetta o quasi perfetta) Locus che contiene due promotori opposti es .: centromeri, trasposoni); molto spesso ci sono regioni del genoma che sono ripetute e anche duplicate in maniera inversa, ed ecco che successivamente alla trascrizione quello che si ottiene è un trascritto che si può ripiegare e Į Trascrizione Trascrizione | appaiare per complementarità di basi; quello che si genera è una sorta di "hairpin" (forcina), processata a dare poi il siRNA. O ancora i siRNA possono anche derivare dalla trascrizione inversa Processamento DICER Processamento DICER di due filamenti del DNA, ottenendo due trascritti che possono appaiarsi tra loro non più come i siRNA hairpin, fornendo in seguito a processamento l'siRNA.
- isiRNA esogeni ("exo siRNA") sono molecole potenzialmente dannose generate durante le varie fasi di un'infezione virale o anche frammenti di RNA di sintesi chimica (quindi ottenuti in laboratorio) iniettati nella cellula a scopo applicativo.
Meccanismo di Silenziamento del Messaggero Target
Come fa la molecola di dsRNA a silenziare il messaggero target? Dal gene nucleare si ottiene un trascritto (sia esso un hairpin o abbia altre forme, ma rimane un dsRNA), il quale è più lungo del siRNA che agisce nella cellula. A questo punto il trascritto viene a contatto con una endonucleasi di nome "Dicer", a generare una molecola di minore dimensione che rappresenta il siRNA a doppio filamento. A seguito del processamento la dsRNA lungo 1) SİRNA 1 Taglio DICER 2) AGO2 RISC AGO2 RISC Formazione del complesso RISC (RNA induced silencing complex) 4) AGO2 AGO2 RISC RISC Taglio del filamento senso 3) Formazione della doppia elica con RNA complementare Degradazione dell'mRNA bersaglio 5)molecola esce dal nucleo e viene a contatto con un grande complesso chiamato RISC (RNA Induced Silencing Complex), al cui interno ci sono una serie di proteine, tra cui la proteina AGO2, che lega la molecola di siRNA e la disaccoppia, in quanto solo uno dei due filamenti agirà sul messaggero bersaglio. L'RNA a singolo filamento è stabilizzato dall'interazione con AGO2 e viene a contatto nel citosol con il suo mRNA bersaglio (si riconoscono con accoppiamento perfetto per complementarità di basi) (vedremo che sarà una differenza con i miRNA). Cosa comporta l'accoppiamento perfetto con il gene target? Per i siRNA la degradazione del messaggero.
Caratteristiche della Molecola dei siRNA
Caratteristiche della molecola dei siRNA:
- È un filamento di RNA a doppia elica lungo 21-23nt con un filamento perfettamente complementare al messaggero bersaglio.
- Ad ognuna delle estremità 3', il filamento è più lungo di due nucleotidi, che rimangono spaiati; al 3' è presente un gruppo -OH terminale mentre al 5' un gruppo fosfato.
- I siRNA si accoppiano con una forte stabilità di appaiamento (detta "High") nella porzione 5' senso (ricca in GC).
- Hanno invece una bassa stabilità di appaiamento nella regione (detta "Low") nella ragione 5' antisenso (ricca di AU); tutto questo è importante nell'ottica di andare a disegnare un siRNA che sia efficace sul trascritto bersaglio che vogliamo inibire.
- Bassa stabilità nella zona centrale dove deve avvenire il taglio della endonucleasi a contatto con il messaggero.
High Low 2-nt overhang 7 5' P .3' OH Helicase + Helicase 3' HO P 5' 2-nt overhang I Queste caratteristiche quindi ci permettono di disegnare, da software predittivi, siRNA aventi come bersaglio specifici mRNA da utilizzare in ricerca e terapia.
Applicazioni dei siRNA in Ricerca e Terapia
Applicazioni dei siRNA: Come anticipato nel precedente paragrafo, in laboratorio possiamo introdurre siRNA (sintetizzati in vitro) o shRNA (short hairpin RNA, precursore a forcina del siRNA, con espressione mediata da un vettore plasmidico/virale) per silenziare in una cellula l'espressione di un gene di interesse mediante: Trasfezione transiente, procedura più veloce perché introduco la molecola precursore del siRNA attraverso complessi siRNA-lipidi, con possibilità di verificare l'effetto di silenziamento sulla proteina di interesse entro le 48/60 ore dal momento della trasduzione/trasfezione; Trasfezione stabile, ovvero trasfettando un vettore plasmidico o trasducendo con una vettore virale la cellula, per selezionare le cellule che hanno inserito nel genoma il vettore, il quale permette di esprimere l'hairpin di un certo siRNA; Infezione virale, quindi infezione delle cellule con vettori virali geneticamente modificati per l'espressione di un shRNA e successiva selezione, un procedimento sicuramente più efficiente rispetto alla trasfezione ed usata per una popolazione di cellule molto resistente alla trasfezione stessa.
Struttura del Vettore per l'Espressione di shRNA
Come deve essere strutturato un vettore, che sia esso virale o plasmidico, per esprimere un piccolo shRNA? Ad un certo punto del vettore si va a clonare la sequenza senso e antisenso intramezzate dalla sequenza che genera il loop; è inoltre posto a monte un promotore che già nella cellula ha la funzione di esprimere piccoli RNA, come ad esempio il vettore U6, efficace sia per la sua costitutività che specificità. Infine, avrà sempre un gene per la resistenza ad antibiotico per cellule eucariotiche se si vuole avere trasfezione stabile.
Sense Strand Loop Antisense Strand - CCGGNNNNNNNNNNNNNNNNNNNNNCTCGAGNNNNNNNNNNNNNNNNNNNNNTTTTT - GGCCNNNNNNNNNNNNNNNNNNNNNGAGCTCNNNNNNNNNNNNNNNNNNNNNAAAAA / U6 cppt hPGK RRE puroR | SIN/3' LTR (*) Psi pLKO.1-puro 7086 bp RSV/5' LTR f1 ori pUC ori ampR Sense Strand 5' - 3' - UU Loop Antisense Strand Figura 1: Vettore plasmidico
siRNA nella Ricerca di Base: Regolazione dell'Espressione Genica
La Prof.ssa spiega come in laboratorio i siRNA siano stati utilizzati nella ricerca di base per regolare l'espressione genica di determinate proteine. In particolare, prende come riferimento la proteina p63, fattore di trascrizione della famiglia p53, la quale è maggiormente conosciuta come "tumor soppressor"; tuttavia il ruolo principale della proteina p63 (seppure coinvolta nella cancerogenesi) è quello di coinvolgimento nella proliferazione delle cellule p63 Coupling between glucose metabolism HK2 Proliferation and mitochondrial function VDAC H2O VDAC H2O2 Glucose IV della pelle, chiamato anche "master gene" del O2 K H2O2 HK2 ADP Glucose ADP ... Glucose-6P 7 ATP H LANT ATP ATP e e" ADP HK2 H. ADP ee 1 02 ATP' H Glucose-6P H differenziamento epiteliale. Nello specifico avevano il sospetto che p63 regolasse l'espressione di un gene che esprime l'esochinasi II (uno dei primi enzimi della 2 H+H N.M. ICI LANTS H' cyto cyto glicolisi) > La glicolisi è uno - p63 expressing cells p63 depleted cells degli step più importanti della proliferazione cellulare, in quanto la cellula ottiene ATP tramite il seguente processo di respirazione cellulare. Nello specifico sono stati raccolti i cheratinociti (cellule proliferanti dello stato basale della nostra pelle), trasfettati con un siRNA diretto contro il mRNA della proteina p63 e valutata l'abbondanza del messaggero nelle cellule, con una diminuzione arrivata anche fino all'80%. Con circa le stesse percentuali è stata rilevata una diminuzione anche dell'esochinasi II, confermando il sospetto iniziale.